STRING数据库的蛋白质相互作用(PPI)网络分析 |
您所在的位置:网站首页 › 基因数据库的作用是 › STRING数据库的蛋白质相互作用(PPI)网络分析 |
STRING数据库的蛋白质相互作用(PPI)网络分析
|
假设我们同样基于表达谱数据获得了一些差异表达的基因列表,现在有待于识别这些基因间的关系。考虑到编码基因发挥作用的最终形式是以蛋白功能实现的,因此就通过STRING数据库搜索这些差异基因间可能的相互作用。
2、输入基因名称列表并指定物种 首先打开STRING数据库(https://string-db.org),点击主页的“SEARCH”。新界面中,选择“Multiple proteins”执行多蛋白间的相互作用分析。输入或上传给定的基因或蛋白名称列表,并在“Organism”中指定物种,然后点击“SEARCH”进入下一步。
3、基因-蛋白关系确认 在新界面中,STRING数据库返回了给定基因对应的蛋白名称,有待进一步确认。默认情况下,直接点击“CONTINUE”继续即可。
4、蛋白互作(PPI)网络获得 然后会在数据库中匹配给定蛋白的相互作用关系,很快即可得到PPI网络了。 网络图中,节点代表各蛋白,节点标签为这些蛋白的名称。节点中的图案代表了该蛋白质的三维结构,如果为空则结构目前未知。若两个蛋白质之间存在相互作用,则以连线连接,连线的颜色反映了互作类型,包括试验验证的或预测得到的,也包含直接物理作用、共表达、基因融合等关系。有关节点和连线的颜色等所代表类型的详细信息,可点击下方“Legend”查看。 在网络图中点击感兴趣的某特定蛋白,将以弹窗展示其名称、结构、功能、物种来源等详细信息。对于表征蛋白互作的连线的描述同样如此,点击感兴趣的连线,将弹窗展示互作两节点的描述,证据来源,互作类型,以及得分值等信息。
5、网络编辑 对于网络图中孤立的不存在任何互作的蛋白,如不期望展示,可在“Setting”的下方选择“hide disconnected nodes in the network”隐藏。 类似地,根据蛋白间的互作类型或互作强度、可信度等,也可在“Setting”中进行一些筛选。例如可选是否展示直接物理互作、共表达、基因融合等类型,或者根据互作得分过滤去除低可信的、强度较弱的互作等。 对于网络整体布局,可以在网络中拖动节点的位置,进行调整。
6、蛋白功能分析 此外,STRING同时还能对网络中的蛋白进行基因本体(GO)富集分析等,提供这些蛋白所参与功能的见解。
7、网络图及蛋白互作关系表的输出 最后对网络图输出保存,或者将识别的蛋白质相互作用关系导出,可点击“Exports”,选择需要的信息下载。
例如这是调整布局后,去除孤立节点并过滤低可信度相互作用的最终网络。
更多内容,请添加“纪伟讲测序”官方公众号,欢迎您的咨询与交流返回搜狐,查看更多 |
【本文地址】
 准备待搜索的基因名称列表
准备待搜索的基因名称列表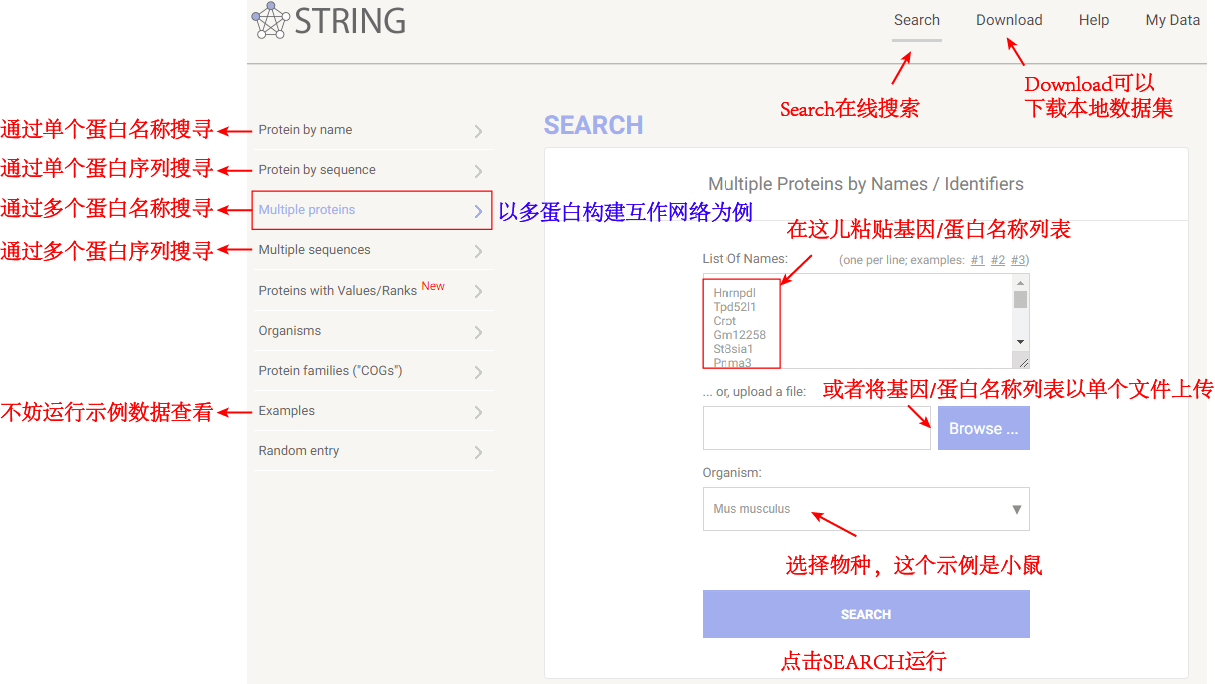 搜索界面及相关设置
搜索界面及相关设置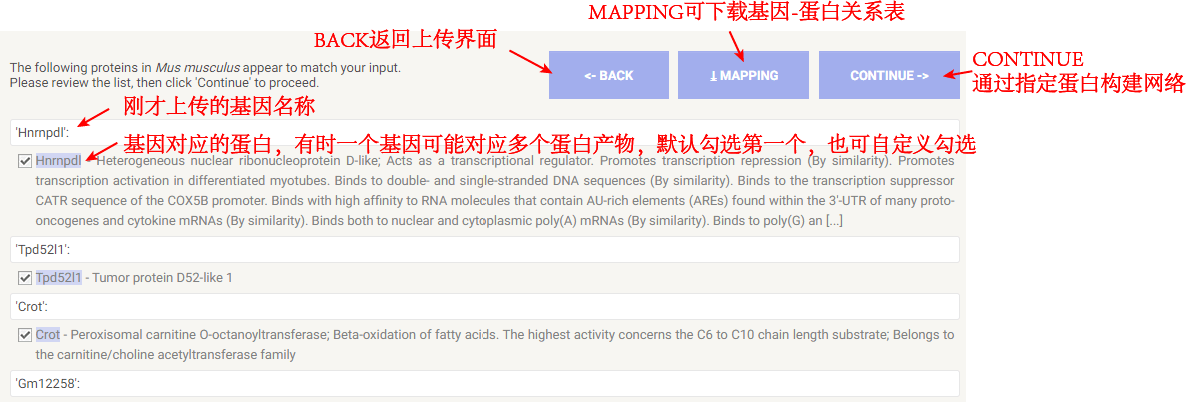 确认基因和蛋白的对应关系
确认基因和蛋白的对应关系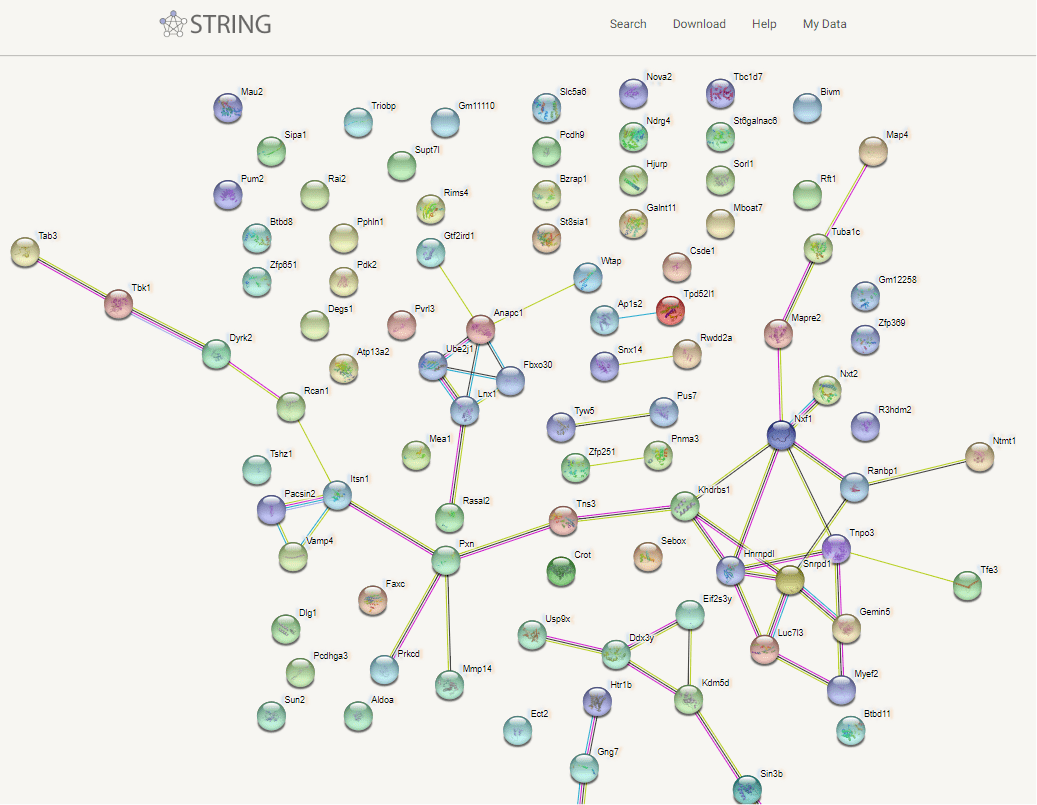 PPI网络图
PPI网络图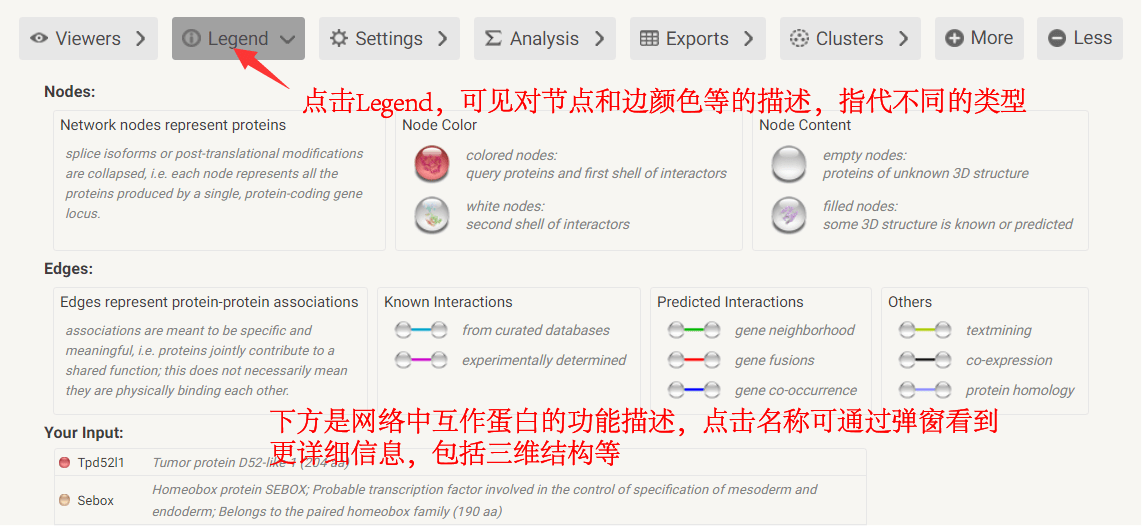 图例中,对蛋白节点和互作类型的描述
图例中,对蛋白节点和互作类型的描述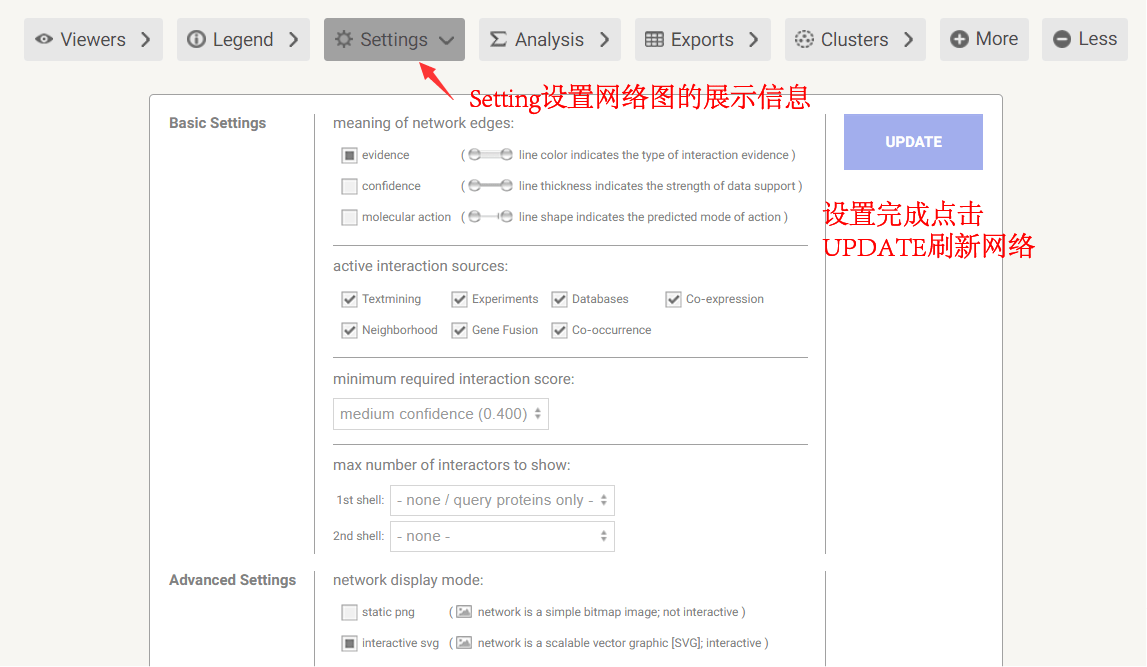 Setting界面可以选择或过滤一些蛋白节点或互作类型
Setting界面可以选择或过滤一些蛋白节点或互作类型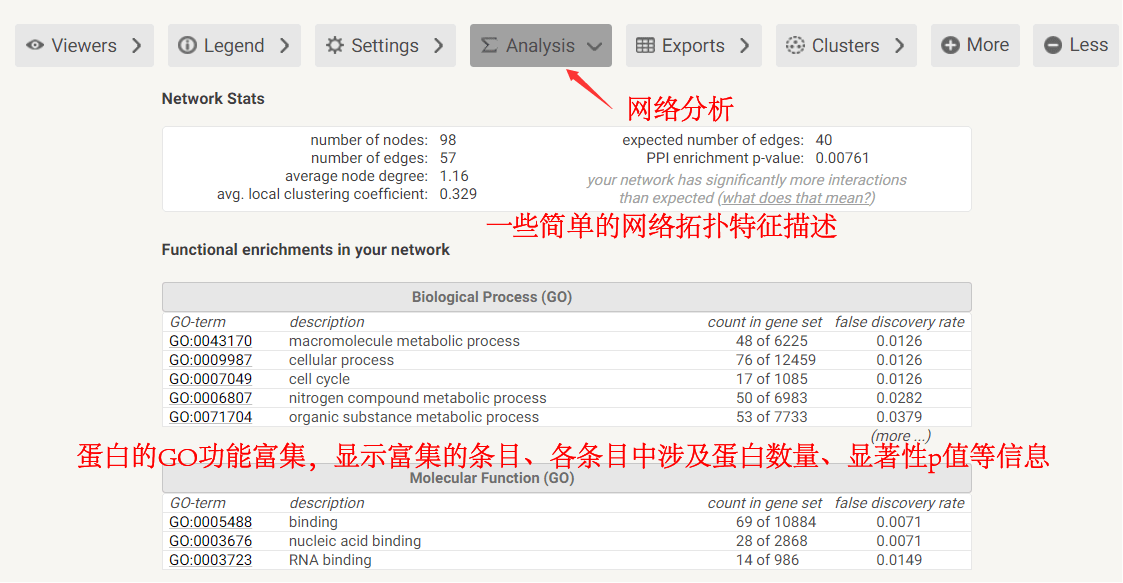 网络中蛋白的GO功能富集分析
网络中蛋白的GO功能富集分析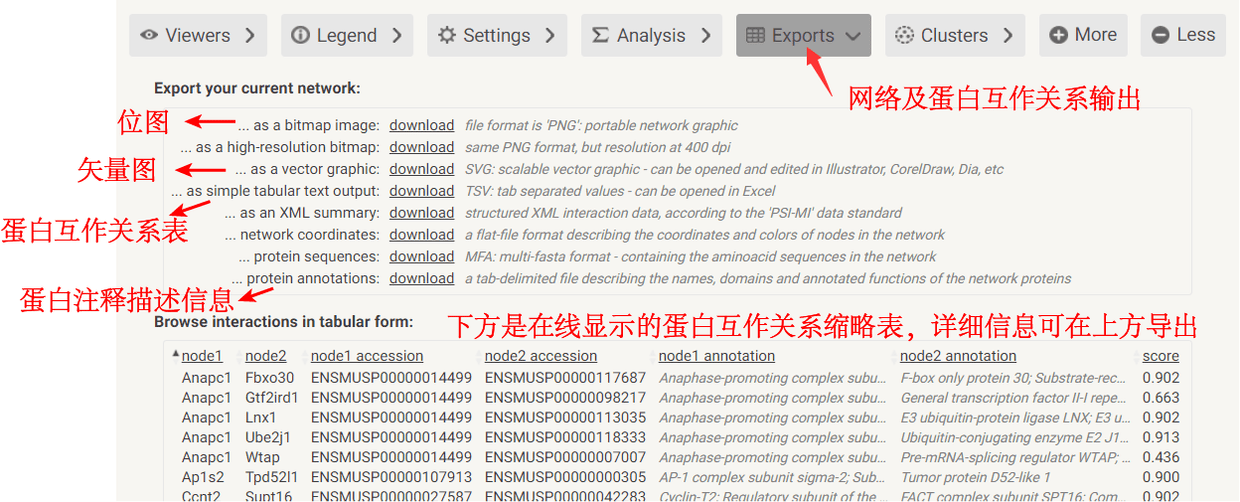 选择下载结果内容
选择下载结果内容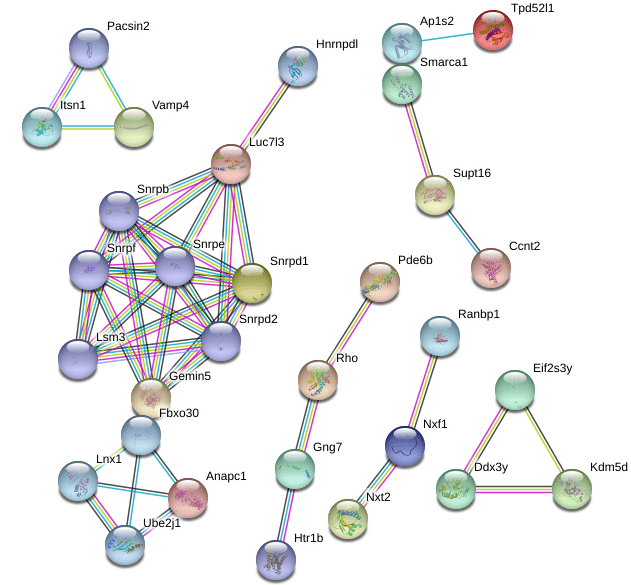 下载后的网络图示例
下载后的网络图示例