跟着Nature Communications学作图:R语言ggtree绘制进化树 |
您所在的位置:网站首页 › 进化树图注 › 跟着Nature Communications学作图:R语言ggtree绘制进化树 |
跟着Nature Communications学作图:R语言ggtree绘制进化树
|
论文 A highly conserved core bacterial microbiota with nitrogen-fixation capacity inhabits the xylem sap in maize plants https://www.nature.com/articles/s41467-022-31113-w 本地pdf s41467-022-31113-w.pdf 数据代码链接https://github.com/PlantNutrition/Liyu 今天的推文我们重复一下论文中的Figure4c的左侧的进化树,右侧的注释信息添加单独出一篇推文介绍 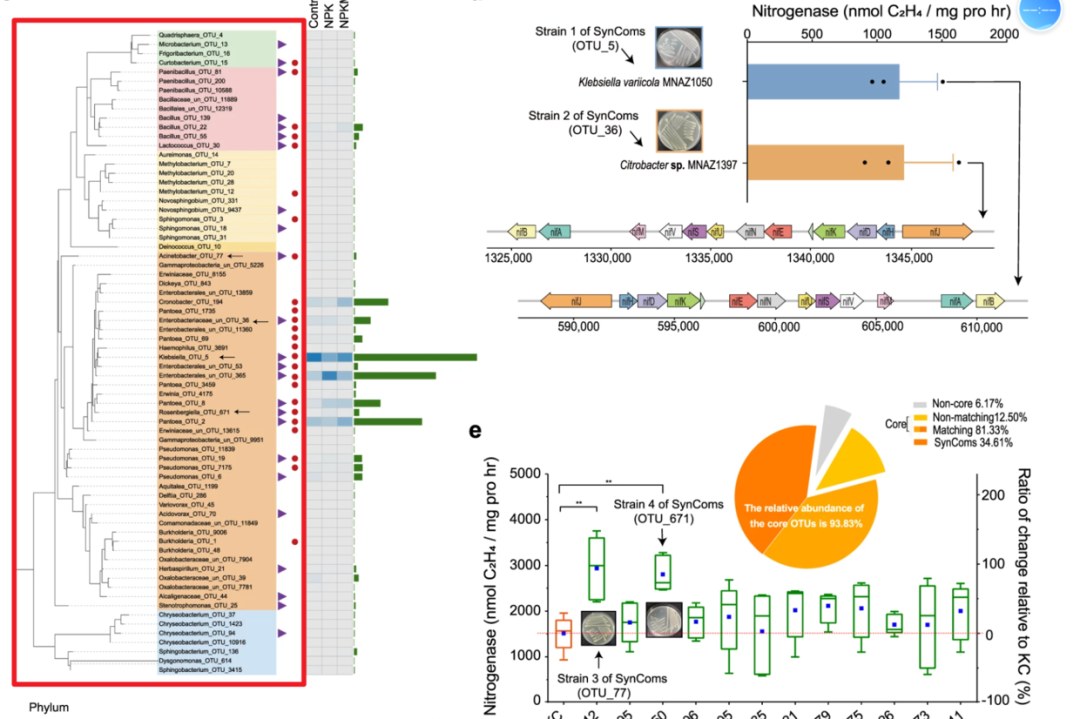 image.png 论文中提供的代码写到作图用到的是ITOL,所有的图都用ggplot2系列的包来做的话,后续拼图就会省去很多麻烦,这里介绍一下用ggtree如何实现这个图  image.png 首先是进化树文件论文中提供的数据我没有找到书文件,有用来建树的fasta文件,论文中构建进化树的方法我也暂时没看懂,这里我用最简单的方式获取树文件,mafft比对,然后iqtree建树(这个方法不一定对) mafft otus_0.01.fa > otus_0.01_aligend.fa iqtree -s otus_0.01_aligend.fa 最基本的进化树展示 library(ggtree) library(treeio) tree% arrange(desc(y))然后使用annotate()函数添加背景颜色,这里正常使用geom_rect()函数应该也可以,但是不知道为什么调节透明度的参数alpha不起作用 ggtree(tree)+ xlim(NA,2.2)+ annotate(geom="rect", xmin=1.7,xmax=2.2,ymin=46.5,ymax=70.5, fill="red", alpha=0.5)+ annotate(geom="rect", xmin=1.7,xmax=2.2,ymin=46.5,ymax=21.5, fill="blue", alpha=0.5)+ annotate(geom="rect", xmin=1.7,xmax=2.2,ymin=0.5,ymax=21.5, fill="green", alpha=0.5)+ geom_tiplab(align = TRUE)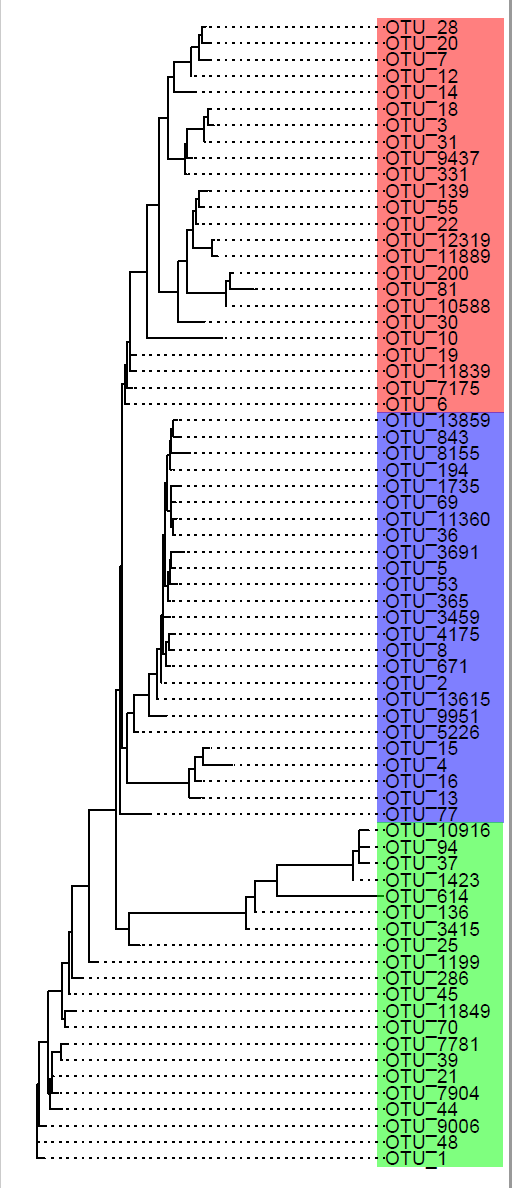
|
【本文地址】