linux利用MEME |
您所在的位置:网站首页 › 转录因子预测meme › linux利用MEME |
linux利用MEME
|
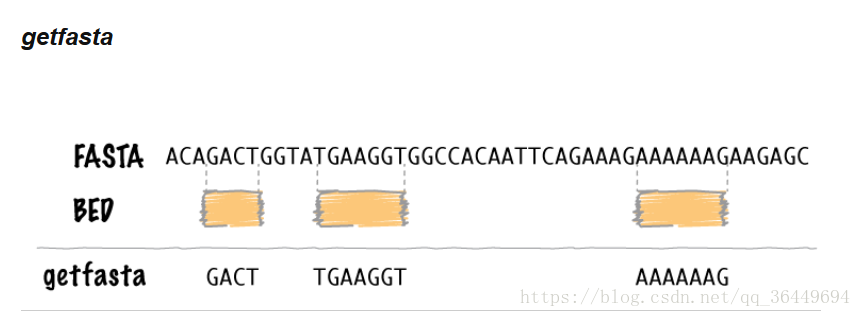
问题来源: 利用MACS进行Peak-calling分析后继续进行motif-analysis,MEME-Chip的输入文件格式要求是fa文件,但是MACS产生的对应文件是bed格式,所以需要将bed文件转成fa文件 解决方法: 1.twoBitToFa 下载地址: http://hgdownload.cse.ucsc.edu/admin/exe/linux.x86_64/ 在linux上安装好后 输入 chmod 744 twoBitToFa (会将文件变成可执行文件,怎么实现的我也不懂) 再执行 twobittofa hg38.2bit hg38.fasta 或者 twoBitToFa -bed=xxxx.bed/leofs/noncode/reference/human/hg19/hg19.2bit out.fa #其中,xxxx.bed为需要转换的文件,/leofs/noncode/reference/human/hg19/hg19.2bit为人类参考基因组hg19.2bit的存储路径,out.fa为输出的文件(可根据需要命名成xxx.fa) 或者 twoBitToFa -bed=T.changhai_ALL_withinIntron_IGR_sigNC.bed ~/zhaogg/rna-seq-data/h19_bowtie_db/genome_all.fa_db.2bit 51T.fa 以上的执行命令都是我搜集到的(百度:如何将bed文件转换成fa文件) 但是不幸的是,并没有什么用(如果你会的话请告诉我 谢谢!) 2.bedtools 或许你会问:“博主你是不是脑子有问题,直接告诉我能使的不就行了么?” “聪明,但是我是一个偏文科的理工科生,所以我习惯了先抑后扬。” 安装: wget https://github.com/arq5x/bedtools2/archive/v2.26.0.tar.gz tar -xvf v2.26.0.tar.gz cd bedtools2-2.26.0 make(编译时间有点长) 代码: bedtools getfasta -fi test.fa -bed test.bed -fo test_out.fa #test.fa是参考基因组 test.bed是要转换的bed文件 test_out是输出的fa文件 ps:一定要在/bedtools2-2.26.0目录下执行 原理: 搞定收工~~ |
【本文地址】
今日新闻 |
推荐新闻 |