手把手教学 |
您所在的位置:网站首页 › 设计引物序列依据 › 手把手教学 |
手把手教学
|
9、当基因存在多个转录本时,最好将sgRNA设计在同源区域。 二、sgRNA的设计 1.NCBI获取基因信息,选择编辑区域 在NCBI主页Gene界面输入基因名称搜索对应的基因。此处以人类KAT7基因为例;
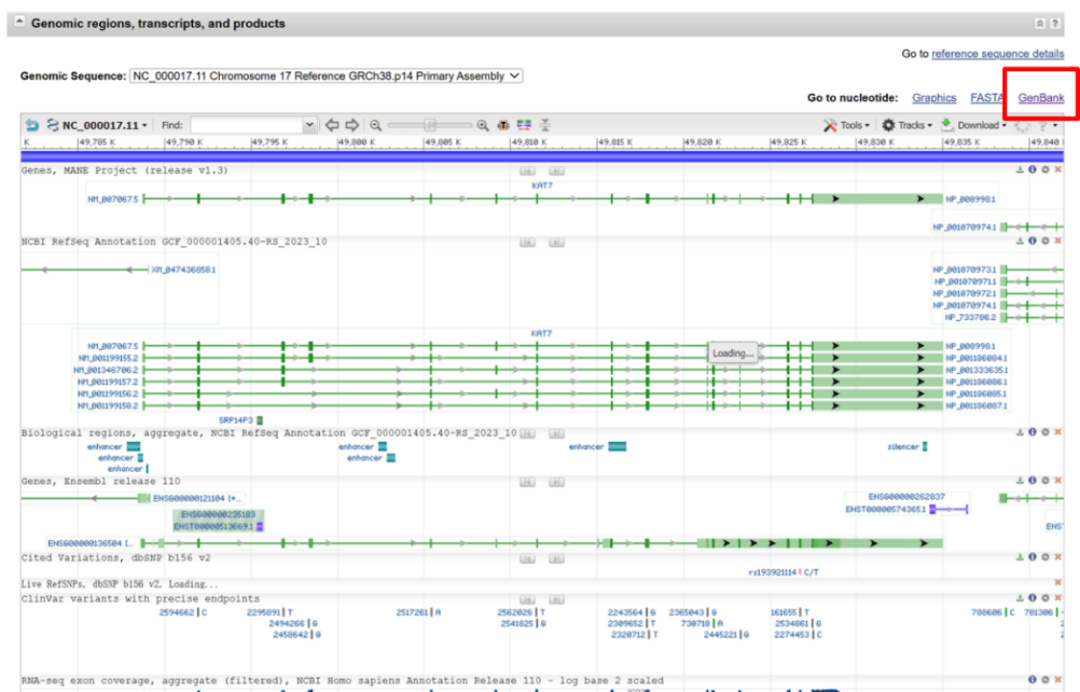
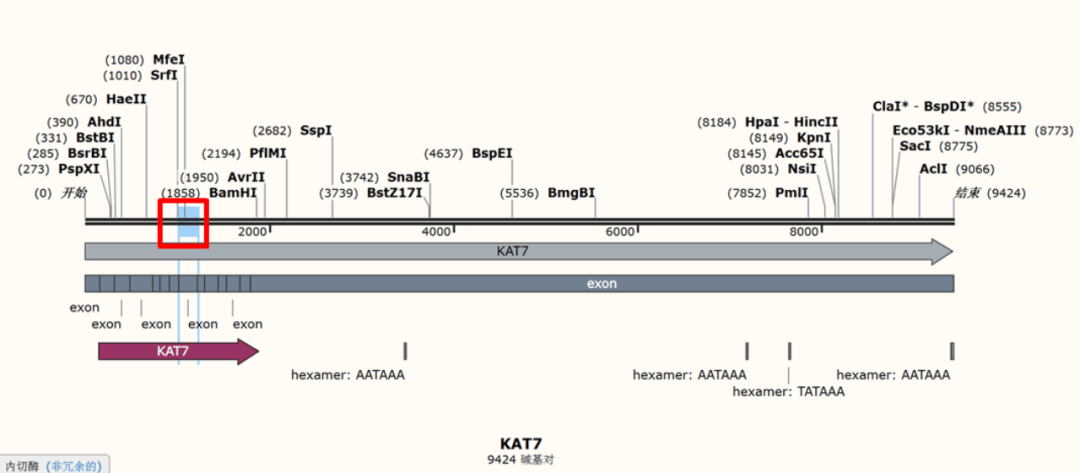
2、点击search后,滚动至“基因组区域、转录本和产物”区域,将能够观察到该基因具有多个转录本,其中竖立的绿色方框表示外显子,每个转录本所共有的方框即为同源区。随后,点击GenBank;
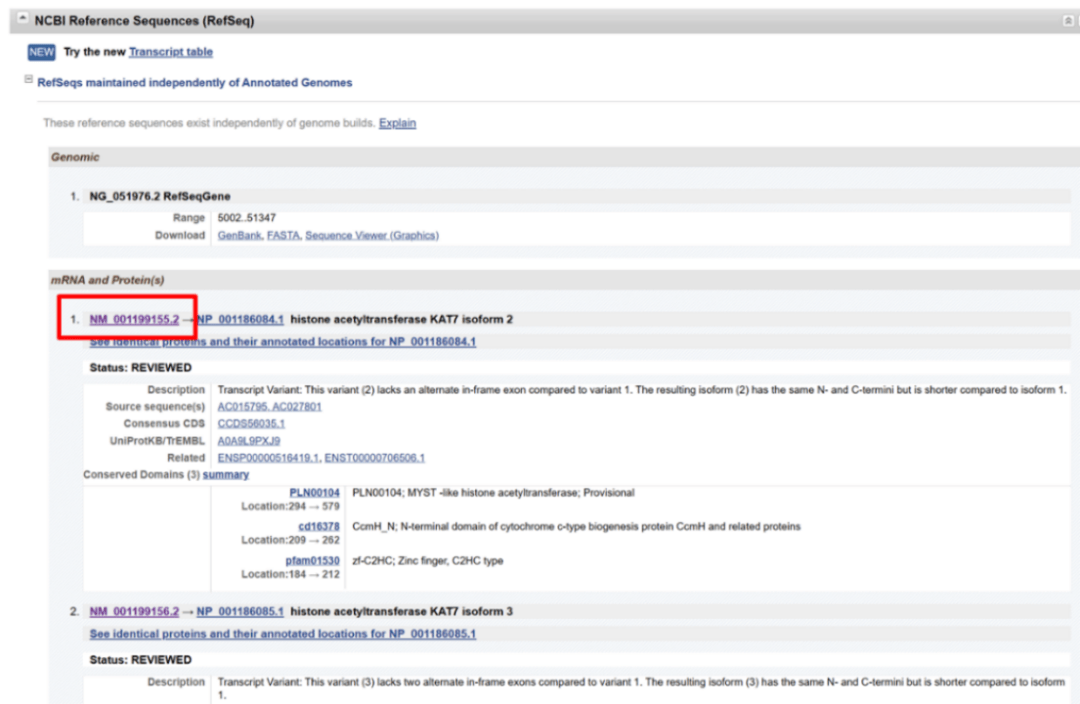
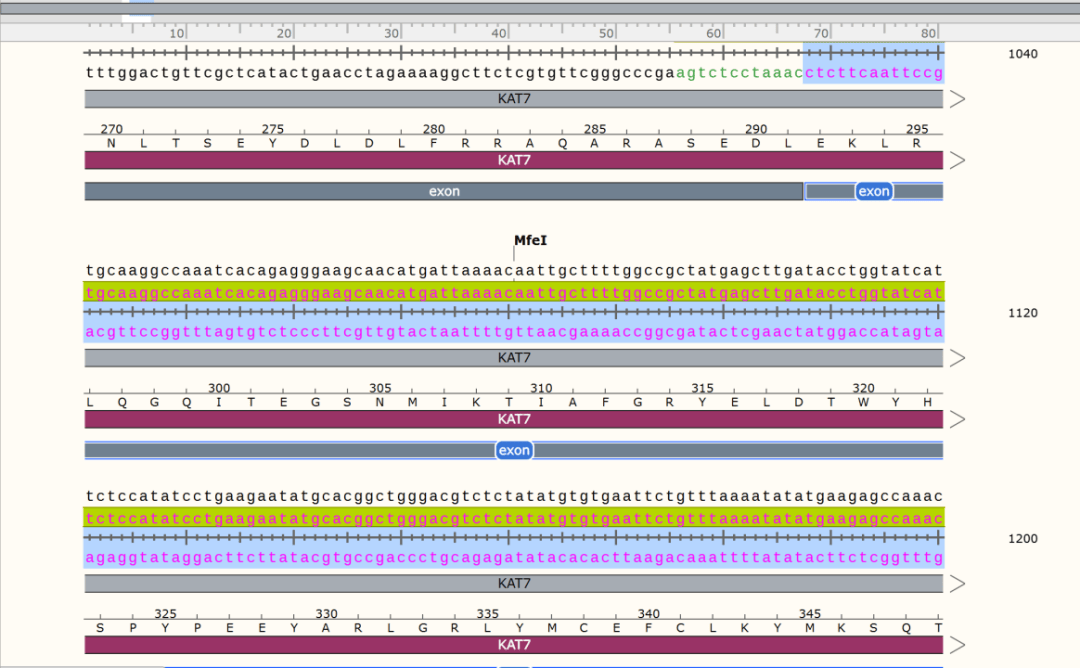
3、下载序列,用snapgene打开,即可查看每个同源区对应的具体碱基序列; 4. 滑动网页至mRNA和蛋白质(s)位置,点击以NM开头的链接即可进入相应转录本的序列,不同NM的条目则表示该基因存在不同的转录本;
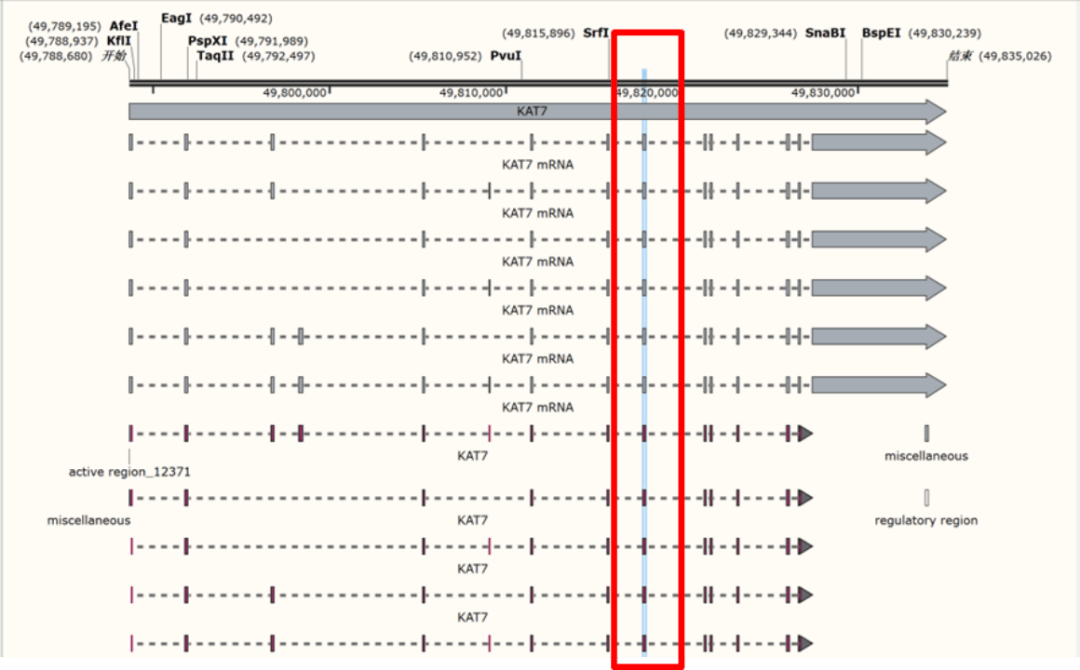
5、点击,下载转录本序列,用snapgene打开; 6、snapgene打开全长序列,找到所有转录本的共外显子。竖立的方框是外显子,在敲除过程中,目标是最大程度地削减KAT7蛋白的表达,以确保转录本的各个亚型均无法表现,因此,应当有针对性地删除这些亚型共享的基因区域,且最佳选择是尽可能靠近CDS区的ATG起始密码子;
7、在转录本序列中查找共外显子序列,找到共外显子所对应的外显子在转录本上的位置,并做出特殊标记;
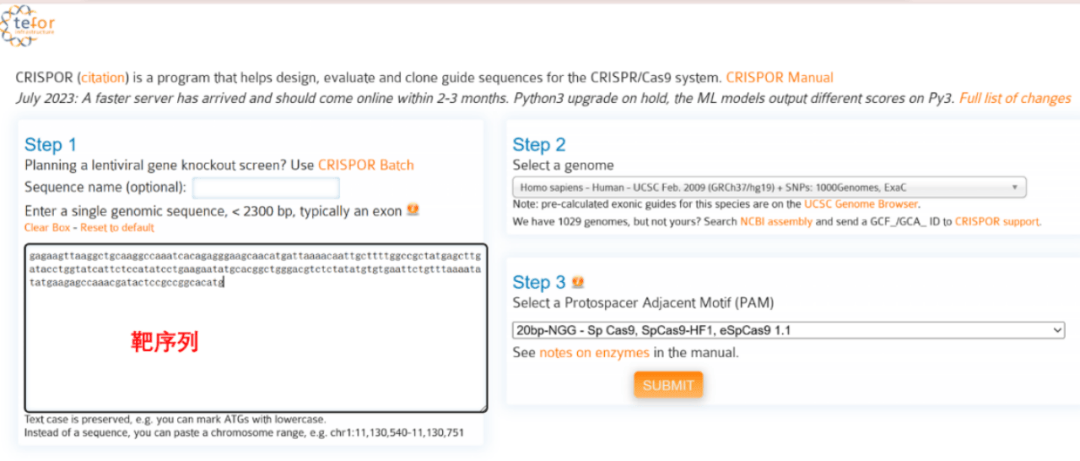
8、复制那段外显子的序列到sgRNA设计网站,http://crispor.tefor.net/(网站有很多);
9、输入上述已选中的同源区域的碱基序列,选择正确的物种和Cas9蛋白;
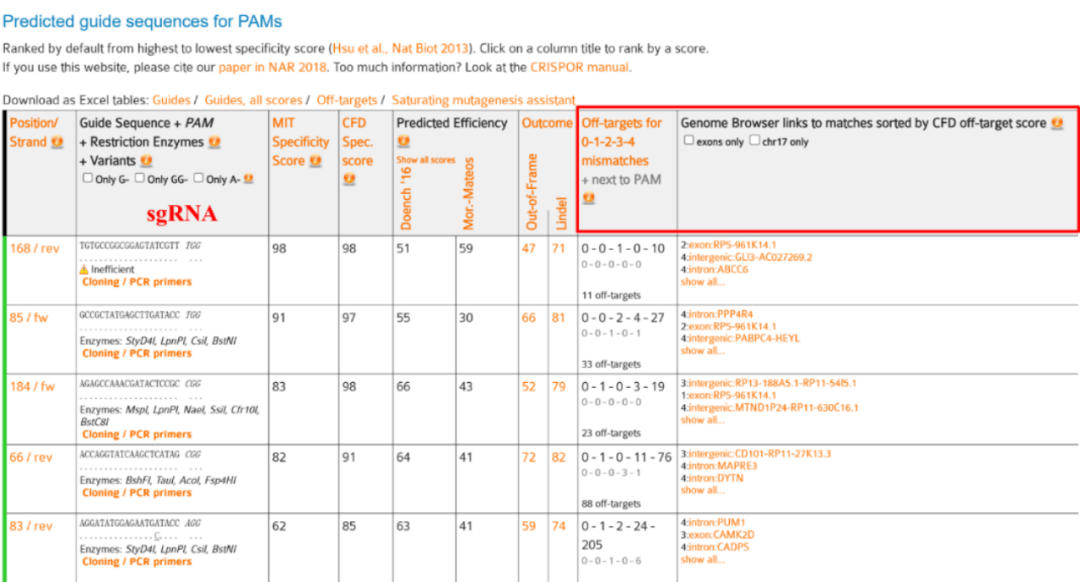
10、网站生成的sgRNA序列信息如下,包括sgRNA序列、PAM、此网站提供的特异性评分、切割效率评分、以及潜在的脱靶具体信息(建议sgRNA设计3-4条,利于高效完成);
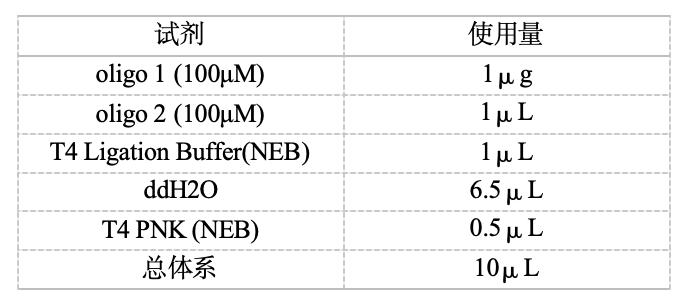
11、设计好的引物送引物公司设计合成。 注意:sgRNA的设计严格按照设计原则进行,需考虑所有候选靶点的序列、位置、正负链、GC含量、潜在的脱靶位点。 三、sgRNA质粒的构建方法 1、酶切载体 LentiCRISPR-V2质粒有两个BsmBI酶切位点,通过使用BsmB内切酶I,我们能够打开所需的区域。酶切条件遵循内切酶说明书,随后进行胶切、回收并备用。 2、寡核苷酸链引物退火 体系:
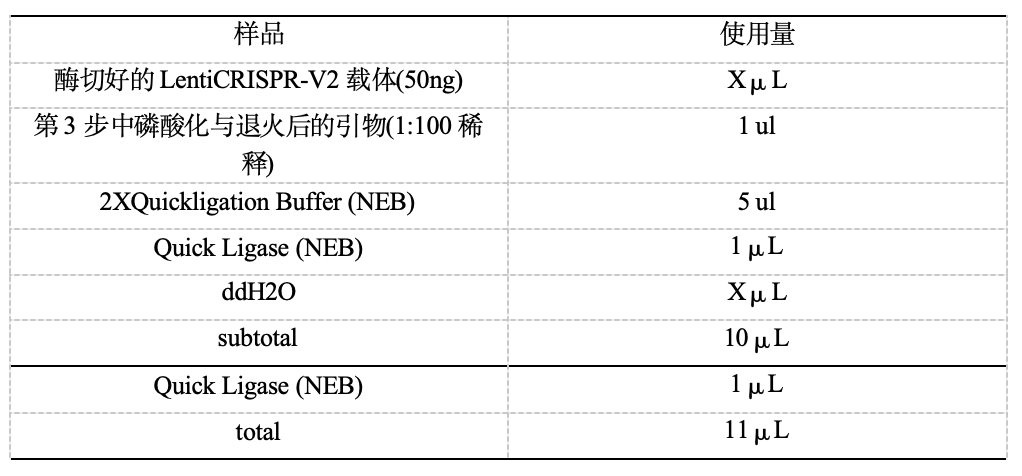
退火参数: 37℃ 30 分钟,95℃ 5 分钟,然后以每分钟降低5℃的速度将温度降到25℃ 3、连接 体系:一般室温放置20-30分钟(NEB的快速T4连接试剂盒)
4、质粒转化: ①从-80℃存储的Stbl3感受态细胞中取出并解冻,将5-10µL连接产物轻柔吹混匀后加入感受态细胞,接着在冰上孵育30分钟; ②冰上孵育后,将感受态细胞放入预调至42℃的水浴锅中进行90秒的热激,然后返回冰上孵育10分钟; ③加入500 μL预热至室温的LB培养基,将混合物置于37℃摇床中摇菌30分钟; ④以3000 r/min离心3分钟,弃掉上清,利用冷却至室温的玻璃棒涂布培养皿(AMP抗性),随后在37℃培养箱中过夜生长。 5、挑取单克隆,摇菌,菌落PCR。 6、对PCR生成物进行琼脂糖凝胶电泳,运用凝胶成像仪进行成像,并挑选阳性菌落将其送往测序公司进行测序鉴定。 7、基于测序结果挑选目标菌落进行扩大培养,提取质粒以备用于后续实验室实验。 返回搜狐,查看更多 |
【本文地址】