不用实验,不会生信,网络药理学套路,赶紧学起来 |
您所在的位置:网站首页 › 网络药理学的目的 › 不用实验,不会生信,网络药理学套路,赶紧学起来 |
不用实验,不会生信,网络药理学套路,赶紧学起来
|
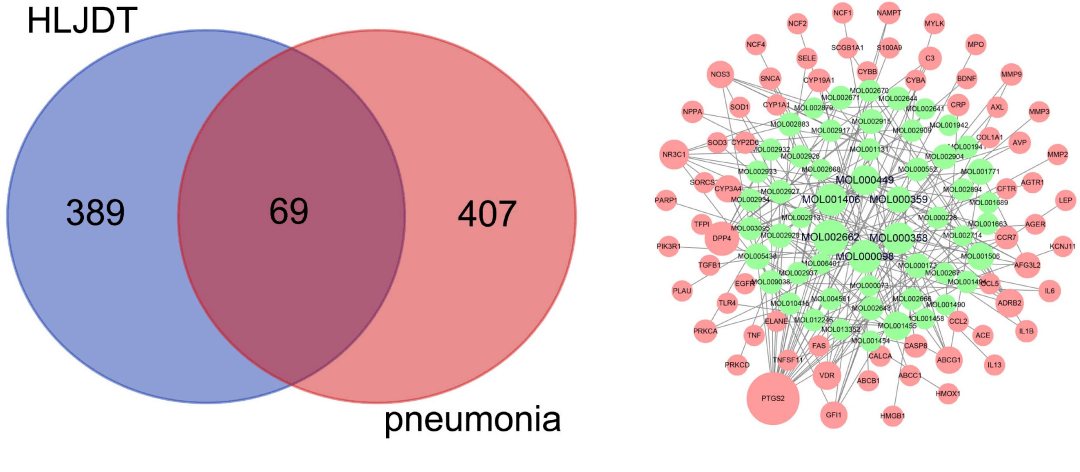
方法与结果 黄连解毒汤中化学成分收集和活性成分筛选 以“Huanglian,” “Huangbo,” “Huangqin,” 和“Zhizi”在TCMSP数据库中查找黄连解毒汤各个中药所含化学成分,并以口服生物利用度(OB)>30和药物相似性(DL)>0.18为原则筛选活性化合物。最终收集到102个活性化合物。 活性成分靶点预测 BATMAN-TCM, STITCH和SwissTargetPrediction三个数据库筛选上述获得的活性化合物。其中BATMAN-TCM score ≥20 和adjusted p ≤0.05。SwissTargetPrediction严格限定物种为“人”和可能性(probability)大于0.6。STITCH限定限定物种为“人”和置信分数(confidence score)≥0.6。最终预测到符合上述的靶点458个。 肺炎相关基因/靶点收集 DrugBank、OMIM、TTD、CTD、GeneCards、NCBI Gene database和 DisGeNET等7个疾病数据库收集肺炎相关靶点信息。以关键词“pneumonia”搜索,最终分别在上述数据库中收集到63, 116, 15, 39, 44, 229和191靶点。删除重复后,最终收集到疾病靶点476个。 交集靶点 将活性成分靶点映射到肺炎相关靶点上,发现两者交集靶点有69个,对应的活性化合物有54个(图3)。
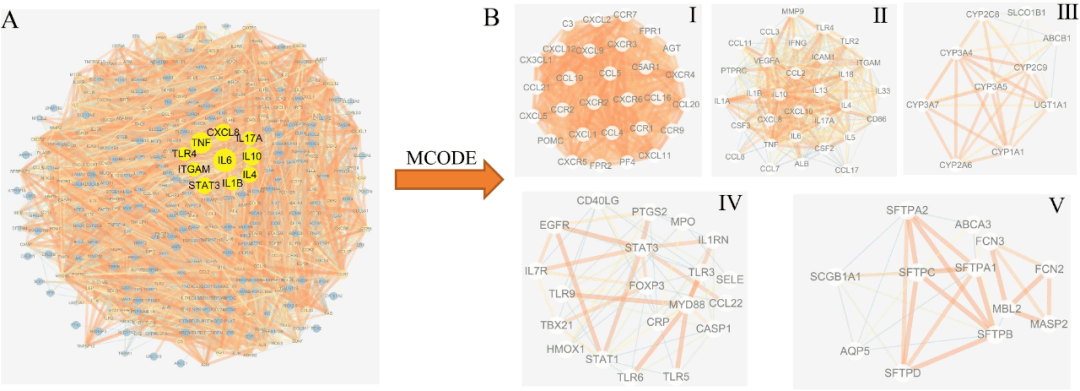
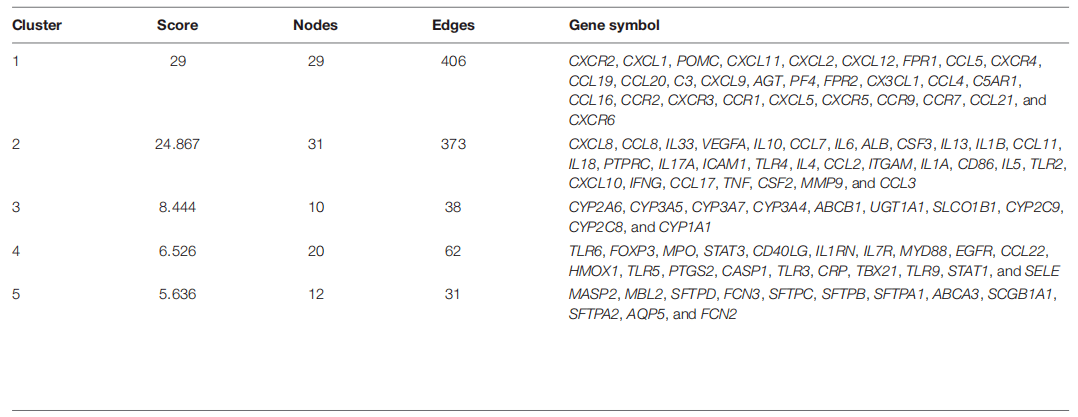
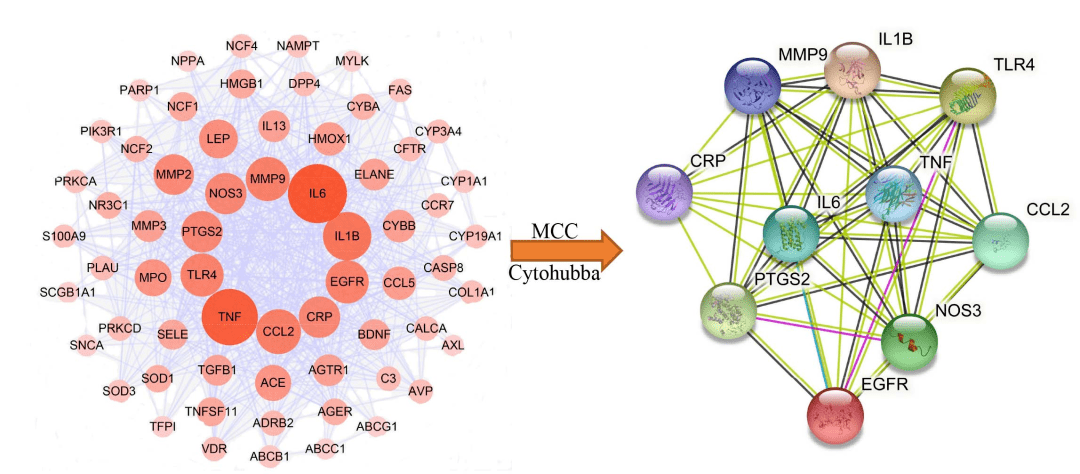
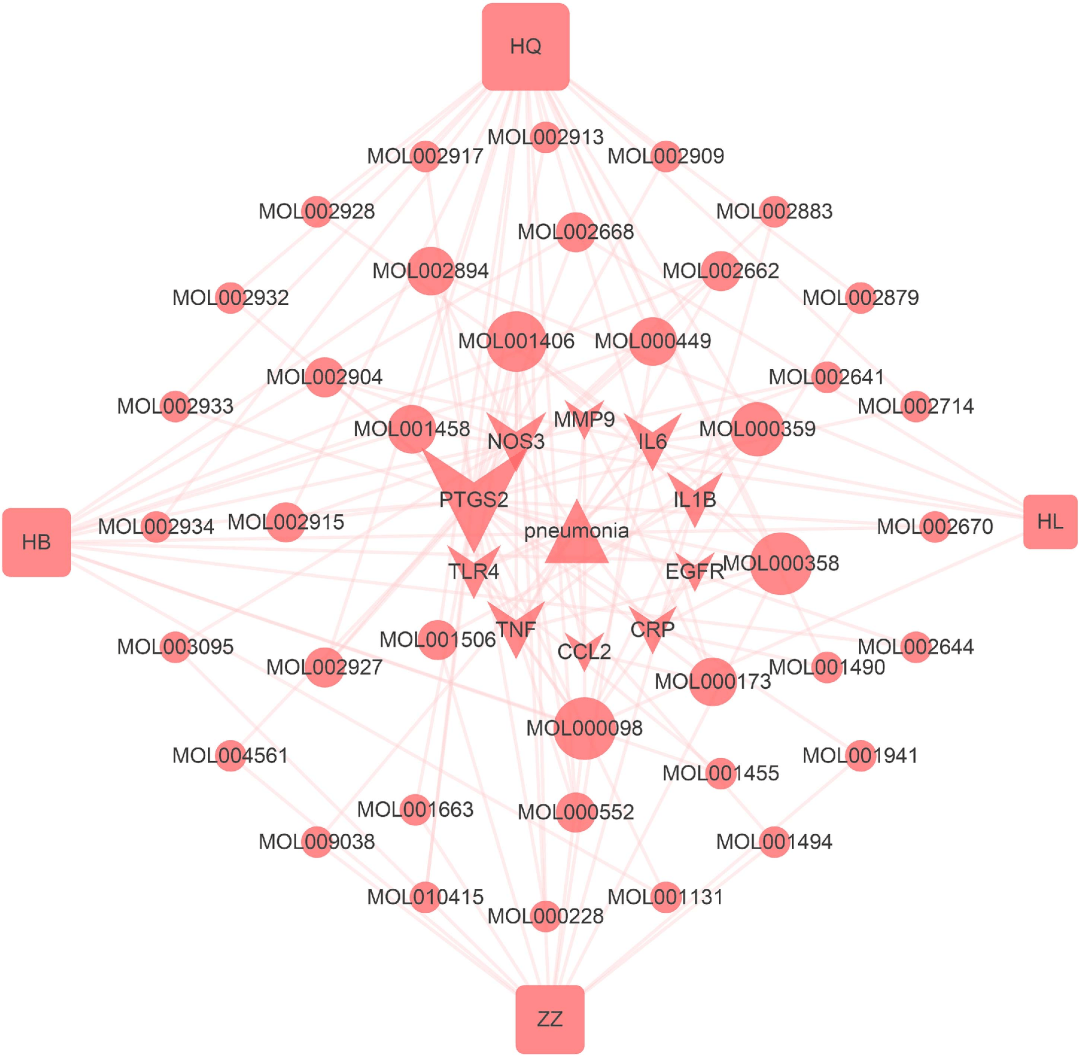
图3. 交集靶点韦恩图和活性成分和靶点网络 网络构建及可视化 作者共建立了4个网络:交集靶点-活性成分网络、疾病PPI网络、交集靶点PPI网络、中药-活性成分-核心靶点-疾病网络。图2B为交集靶点-活性成分网络。以度值(>=7)大小为原则,筛选网络中比较重要的活性化合物,发现槲皮素、吴茱萸次碱、谷甾醇、β-谷甾醇、藏花酸和豆甾醇等6个重要的活性化合物。 将上述肺炎相关靶点带入STRING数据库,以物种“人”和置信分数≥0.4为条件构建PPI网络,并将结果导入Cytoscape。图4为疾病PPI网络。其中TLR4, TNF,CXCLB, IL1B, IL17A, IL10, IL4, IL6, STAT3和ITGAM等10个基因度值最大。接着对肺炎PPI网络进一步分析,采用MCODE模块以score cutoff =0.2, k core=2, maximum depth = 100和degree cutoff=2为条件进行聚类分析。共得到16个,取分值最高的前5个聚类(图4B, 表1)。 上述交集靶点带入STRING数据库,以物种“人”和置信分数≥0.4为条件构建PPI网络,并将结果导入Cytoscape。图5为交集靶点PPI网络。其中节点越大,说明度值也越大。 作者还构建了中药-活性成分-核心靶点-疾病网络。网络共包含4种中药, 39个活性成分, 10个核心靶点和1种疾病。发现槲皮素、吴茱萸次碱、谷甾醇、β-谷甾醇、藏花酸和豆甾醇等6个活性化合物在网络节点较大,是比较重要的活性化合物。这与在交集靶点-活性成分网络中发现的一致。
图4. 肺炎PPI网络和聚类分析
表1. 肺炎PPI聚类分析相关信息
图5.交集靶点PPI网络及核心靶点筛选
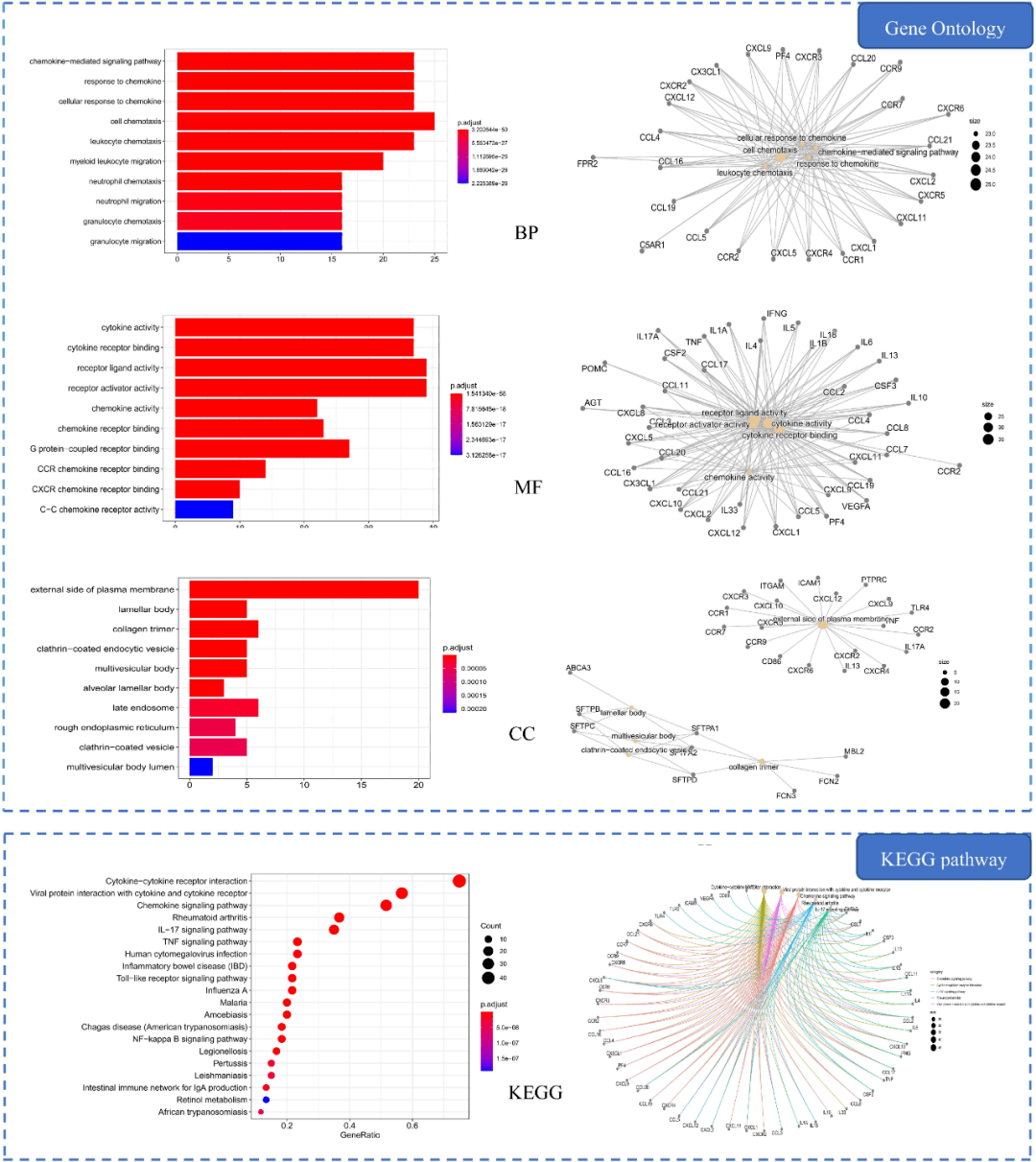
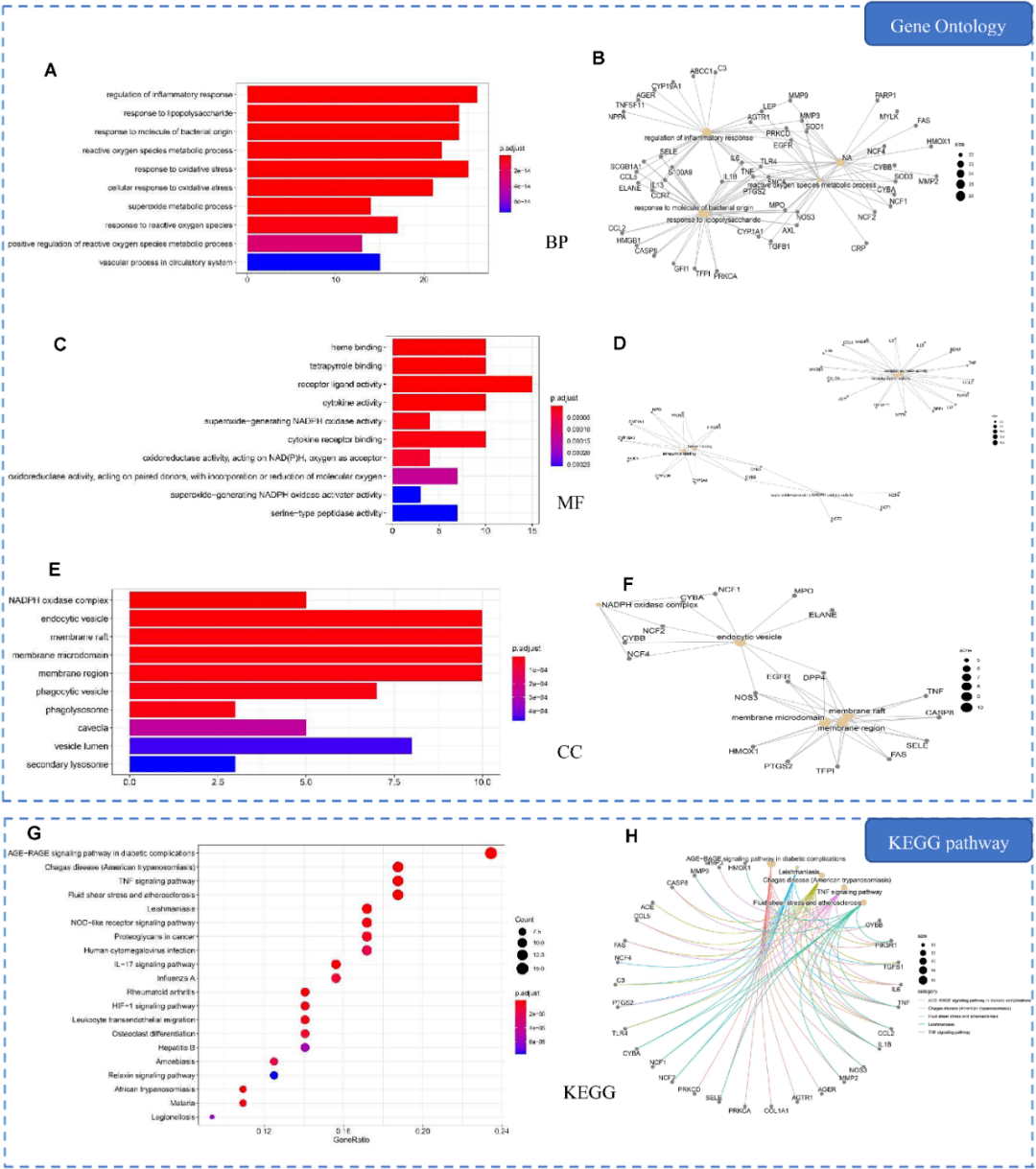
图6. 中药-活性成分-核心靶点-疾病网络图 核心靶点筛选 将交集靶点PPI网络进一步分析,利用插件Cytohubba采用maximum neighborhoodcomponent (MNC)方法筛选,以MNC值最大的10个基因为本网络的核心靶点(图5)。结果提示IL1B, IL6, CCL2, MMP9, PTGS2, TNF, CRP, EGFR, TLR4等10个靶点的MNC值最大,其中TLR4, TNF, IL1B和IL6等4个靶点还是肺炎中比较重要的靶点。 生物学分析 生物学分析包括两方面:GO分析和KEGG通路富集分析。GO分析包括生物学过程(BP)、细胞组分(CC)和分子功能(MF)三个方面。R软件clusterProfiler进行分别对肺炎相关靶点和交集靶点进行生物学分析。其中肺炎涉及1,475 BPs, 99 MFs, 46 CCs和91 KEGG 信号通路(p≤ 0.05),KEGG分析显示通路主要富集在细胞因子受体相互作用, 趋化因子信号通路和病毒蛋白与细胞因子及其受体相互作用。 图7显示的是肺炎相关靶点最显著的生物学分析结果。其中交集靶点共涉及1,730 BPs, 110 MFs, 53 CCs和88 KEGGs (p≤0.05),信号通路主要富集在糖尿病并发症AGE–RAGE 信号通路,恰加斯病(美洲锥虫病)和TNF信号通路等。图8显示的是交集靶点最显著的生物学分析结果。
图7. 肺炎相关靶点生物学分析
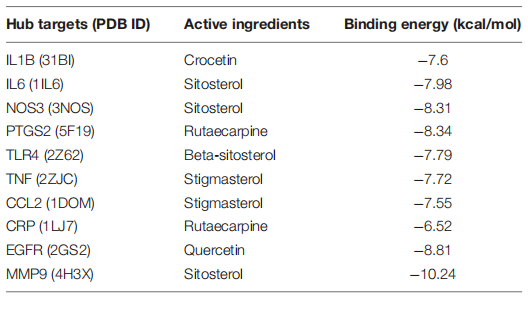
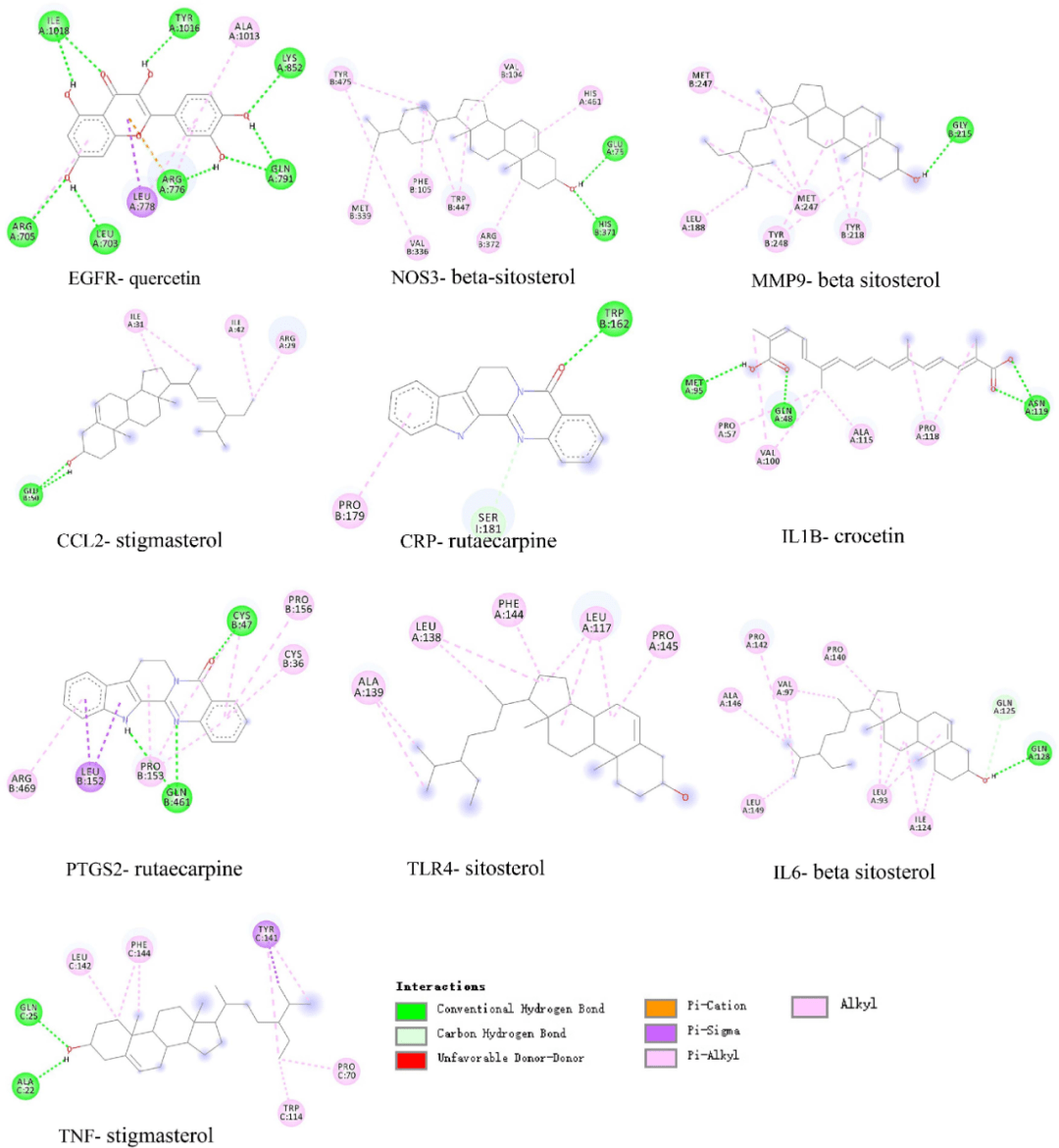
图8. 交集靶点生物学分析 分子对接验证 RCSB PDB网站下载核心蛋白结构,活性成分构象下载自TCMSP,AutoDock 4.2.6去除水分子、配体、加极性氢和加电荷等处理,Discovery Studio进行分子对接。表2显示核心化合物和核心靶点之间分子对接的结果。表2显示核心活性成分与核心靶点之间的结合能大小。结果显示所有结合能都小于−5.0 kcal/mol,提示活性成分和核心靶点之间有较稳定的结合。图9显示的是核心活性成分和核心靶点之间的相互作用。结果显示活性成分和靶点之间存在多种相互作用,包括氢键等。
表2. 核心活性成分和核心靶点之间的结合能
图9. 核心活性成分和核心靶点分子对接图 综合以上,网络药理学要想学习还是比较简单的,比较重要的是学会如何合理的利用相关数据库和软件的使用。学好网络药理学的套路,你也可以轻松发SCI论文。 END 征 稿 启 事 “医学方”始终致力于服务“医学人”,将最前沿、最有价值的临床、科研原创文章推送给各位临床医师、科研人员。 医学方已推出“ 实验室基础”“ SCI写作技巧”“ 文献精读与解析”“医学英语轻松学”“国自然基金申请”“临床数据挖掘”、“基因数据挖掘”、“R语言教程”、“医学统计学”、“微创动物实验培训”等多个专题课程,如需了解课程详细推文,可关注“医学方”公众号,点击“精品专题”进入 腾讯课堂:https://medfun.ke.qq.com 你的每个赞和在看,我都喜欢! 返回搜狐,查看更多 |
【本文地址】
今日新闻 |
推荐新闻 |