Anaconda的安装、配置与使用conda安装软件 |
您所在的位置:网站首页 › 安装conda › Anaconda的安装、配置与使用conda安装软件 |
Anaconda的安装、配置与使用conda安装软件
|
利用conda快速安装软件
安装软件与使用软件是计算生物学需要掌握的技能,大部分的软件都是命令行软件。早先的时候安装软件特别麻烦,现在出了很多自动安装软件的框架,例如conda。起初这个框架只是为了方便安装Python 版本与Packages,但是后来无论是C/C++或者R 之类的运行环境也都能安装了。它有一些已经打包好的安装了各种软件的发行版,例如Anaconda。 1.安装conda可以去anaconda官网下载最新版本,或者去镜像源站下载anaconda的历史稳定版本,也可以安装更小型的miniconda。 由于最新版本总是容易出现版本不匹配的问题,最好选择去镜像源下载稳定版本。 由于运行不同的软件或代码时,需要的环境往往不同,因此,我们需要创建不同的环境方便管理各个库和包的版本。 第一步,在窗口中输入下面这一行代码,创建一个名为python38的虚拟环境,该环境用到的python版本为3.8。(当然,随着不同软件的需要,你可以创建很多不同环境名称和不同python版本的环境。) conda create --name python38 python==3.8输入y进行安装python3.8,当出现下图,表示python38环境创建完成。 可以看到命令行最前面的括号从一开始的默认(base)变成了当前环境的名字(python38),就表示现在就来到了python38环境,在这个环境下安装的库和包的版本,不会影响到其他环境。 在使用conda安装前,需要注意,由于外网网速的限制,我们需要提前添加一些国内镜像源,不然conda下载软件的速度会非常慢。如果需要还原为原始通道,输入conda config --remove-key channels。(这里不需要) 在命令行复制输入以下代码回车,为conda添加上国内镜像源。 conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/main/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/free/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/conda-forge/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/msys2/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/bioconda/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/menpo/ conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/pytorch/ conda config --set show_channel_urls yes使用conda info看看是否已经改好了。 删除某个频道 conda config --remove channels https://...添加完路径后,接下来就是安装软件,这里以常用的计算生物学软件为例,比如blast, mafft 和 bwa/tophat/tophat2。 但是在使用conda 安装blast的时候,遇到了安装非常慢的问题(一直转圈),感觉是因为这些包没有windows版本的原因。于是,决定还是在WSL2 linux虚拟机上,重复上面操作,提前添加一个bioconda的镜像源,在linux上安装软件。 安装blastBLAST包括blastn, blastp, blastx, tblastn, tblastx等。 输入conda install blast安装blast。 多序列比对在生物信息分析中是常用到的操作,目前多序列比对的软件较多,没有一款十分完美的多序列比对工具。有文献报道: 在比对速度上(Muscle>MAFFT>ClustalW>T-Coffee)在比对准确度上(MAFFT>Muscle>T-Coffee>ClustalW)输入conda install mafft安装mafft,并输入mafft -h查看是否完成安装以及使用方法。 bwa是一款DNA-seq比对工具。大部分搞全基因组或者全外的似乎都使用BWA作比对。 输入conda install bwa安装bwa,运行 bwa -h查看是否完成安装。 选择版本更新的tophat2进行安装,tophat2是一款RNA-seq比对工具。 发现tophat官网上,都是python2.7的版本,基本停止更新了。
然后新建并进入到tophat文件夹。 下载完成。
后来发现也可以直接conda install tophat安装tophat!然后通过whereis tophat找到tophat文件,cd到该文件夹,并使用vi tophat命令进入vim编辑器,按a进入编辑模式,将第一行的#!/usr/bin/env python替换成刚刚创建的python2环境的路径,比如/home/zw/miniconda3/envs/python27,按Esc后:wq保存退出,再次运行tophat2。 这次安装生信软件,发现搭建环境还是蛮困难的,尤其是软件都没有提供windows版本的情况下,即使conda添加了镜像源,也没法安装。还是需要在linux或者macos的操作系统上,安装更加友好,甚至一气之下都想买个macbook耍耍了。最后想到电脑里有wsl2的linux,解决了这个问题。 此外,CSDN提供的博客大多重复且过时,希望社区能改进。最后还是需要通过自己看文件的本质是什么,来进行debug。跑通即胜利! |
【本文地址】
今日新闻 |
推荐新闻 |
 这里我选择了2020年11月的windows版本下载并安装,一路next就好。
这里我选择了2020年11月的windows版本下载并安装,一路next就好。  完成安装后,开始菜单栏里出现Anaconda3及一系列的应用软件。
完成安装后,开始菜单栏里出现Anaconda3及一系列的应用软件。  可以点击Anaconda Prompt进入一个类似cmd的命令行框,进行后续操作。
可以点击Anaconda Prompt进入一个类似cmd的命令行框,进行后续操作。 
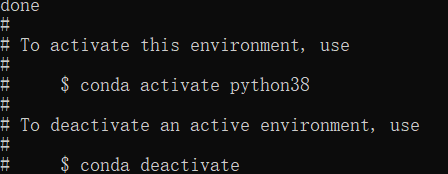 第二步,激活刚才创建的名为python38的虚拟环境。
第二步,激活刚才创建的名为python38的虚拟环境。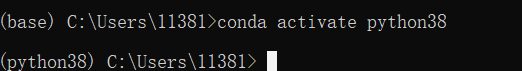 可以通过conda list 查看该环境下安装的库和包的版本。
可以通过conda list 查看该环境下安装的库和包的版本。  可以通过conda env list查看存在哪几个不同的环境。
可以通过conda env list查看存在哪几个不同的环境。 
 查看已安装的镜像源
查看已安装的镜像源 输入blastn/blastp/blastx/tblastn/tblastx -h查看是否完成安装及使用方法。
输入blastn/blastp/blastx/tblastn/tblastx -h查看是否完成安装及使用方法。



 因此,需要另外创建一个Python版本为2.7的环境(这里我已经创建过了)。
因此,需要另外创建一个Python版本为2.7的环境(这里我已经创建过了)。  首先运行conda install -y bowtie2安装bowtie2。
首先运行conda install -y bowtie2安装bowtie2。 先输入wget命令,下载到官网上的压缩包。
先输入wget命令,下载到官网上的压缩包。 再解压文件夹。(gz文件才需要多加个z)
再解压文件夹。(gz文件才需要多加个z) 输入 sudo vim /etc/profile打开PATH添加文件。 在末尾添加export PATH="/mnt/c/11381/tophat/bin:$PATH"将tophat添加到PATH。
输入 sudo vim /etc/profile打开PATH添加文件。 在末尾添加export PATH="/mnt/c/11381/tophat/bin:$PATH"将tophat添加到PATH。 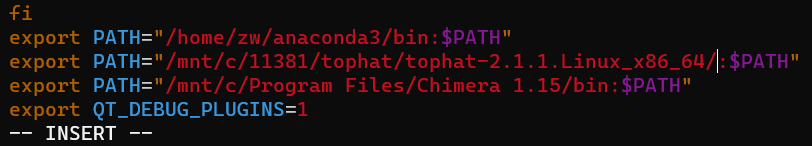 按网上教程输入tophat2即可运行
按网上教程输入tophat2即可运行  但我发现这样做还是会报错。
但我发现这样做还是会报错。 
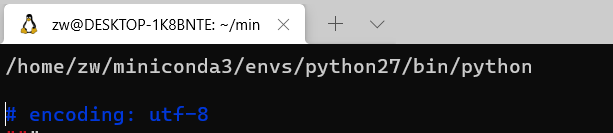 但发现这种实际也有问题,其实就是进入到了python中。
但发现这种实际也有问题,其实就是进入到了python中。  后来一看tophat其实就是个py文件,那我将tophat前面注释掉,运行时输入 python2 tophat不就可以运行起来了。
后来一看tophat其实就是个py文件,那我将tophat前面注释掉,运行时输入 python2 tophat不就可以运行起来了。 