R语言广义线性混合模型GLMMs在生态学中应用可视化2实例合集 |
您所在的位置:网站首页 › 如何做可视化图形模型视频 › R语言广义线性混合模型GLMMs在生态学中应用可视化2实例合集 |
R语言广义线性混合模型GLMMs在生态学中应用可视化2实例合集
|
分析师:Kaizong Ye,Colin Ge 在生态学研究领域,广义线性混合模型(Generalized Linear Mixed Models,简称GLMMs)是一种强大的统计工具,能够同时处理固定效应和随机效应,从而更准确地揭示生态系统中复杂关系的本质(点击文末“阅读原文”获取完整代码数据)。 随着数据分析技术的不断发展,R语言已成为生态学家们进行数据分析的首选工具之一,而GLMMs在R语言中的实现与应用也日益受到关注。 相关视频 本文旨在通过2个实例,帮助客户展示R语言中广义线性混合模型在生态学中的应用及其可视化方法。 1.广义线性混合模型(Generalized Linear Mixed Models,GLMMs)在生态学中的应用广义线性混合模型(Generalized Linear Mixed Models,GLMMs)在生态学中的应用以及如何在R中实现它们是一个广泛且深入的主题。这类模型是线性混合模型(Linear Mixed Models,LMMs)和广义线性模型(Generalized Linear Models,GLMs)的自然延伸,它们提供了在存在随机效应时,对响应变量与预测变量之间关系进行建模的灵活性。 在生态学中,广义线性混合模型的应用特别广泛,这主要得益于它们在处理复杂数据结构、考虑随机效应以及解释非线性关系方面的能力。例如,在种群动态、群落组成、物种分布等研究中,广义线性混合模型经常被用来解释和预测各种生态现象。 这篇文章主要是为了展示如何拟合GLMM、如何评估GLMM假设、何时在固定效应模型和混合效应模型之间做出选择、如何在GLMM中进行模型选择以及如何从GLMM中得出推论的R脚本。 使用数据(查看文末了解数据免费获取方式)如下:  以下是一个R脚本的示例,用于展示如何在广义线性混合模型(GLMM)中演示GLMM的拟合、假设检验、模型选择以及结果推断。我们将使用lme4和arm包进行混合模型的分析,并使用RCurl包来下载示例数据集。 最终得到以下的模型预测图 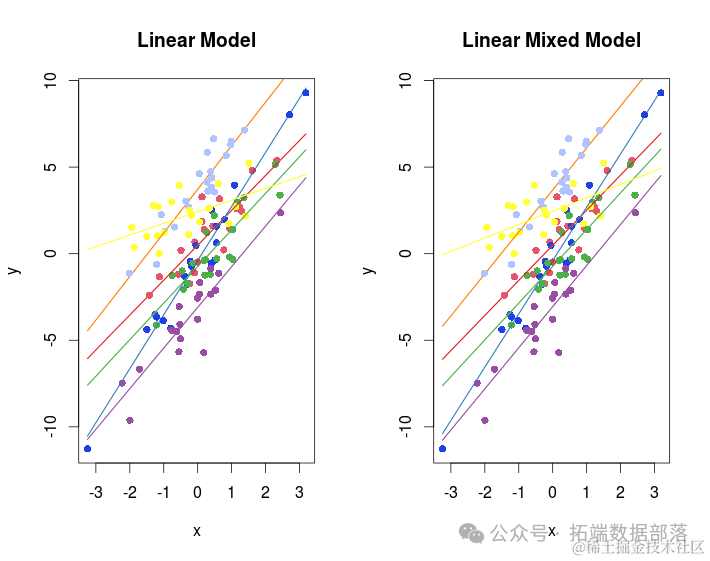 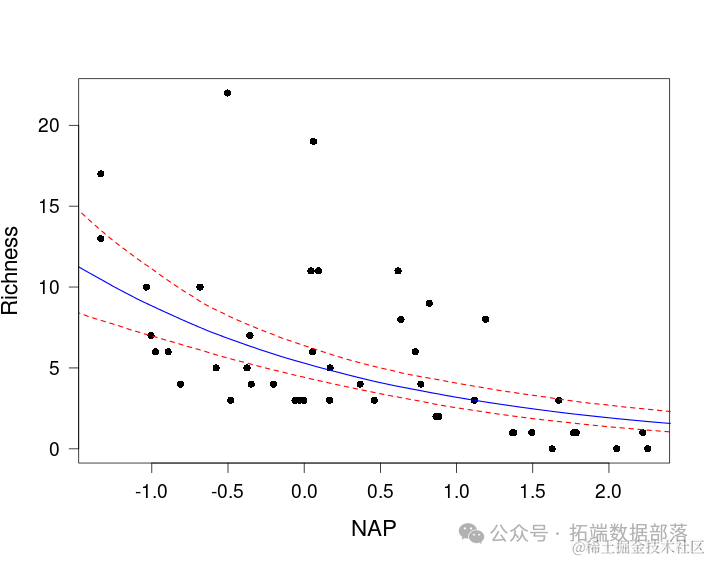 01 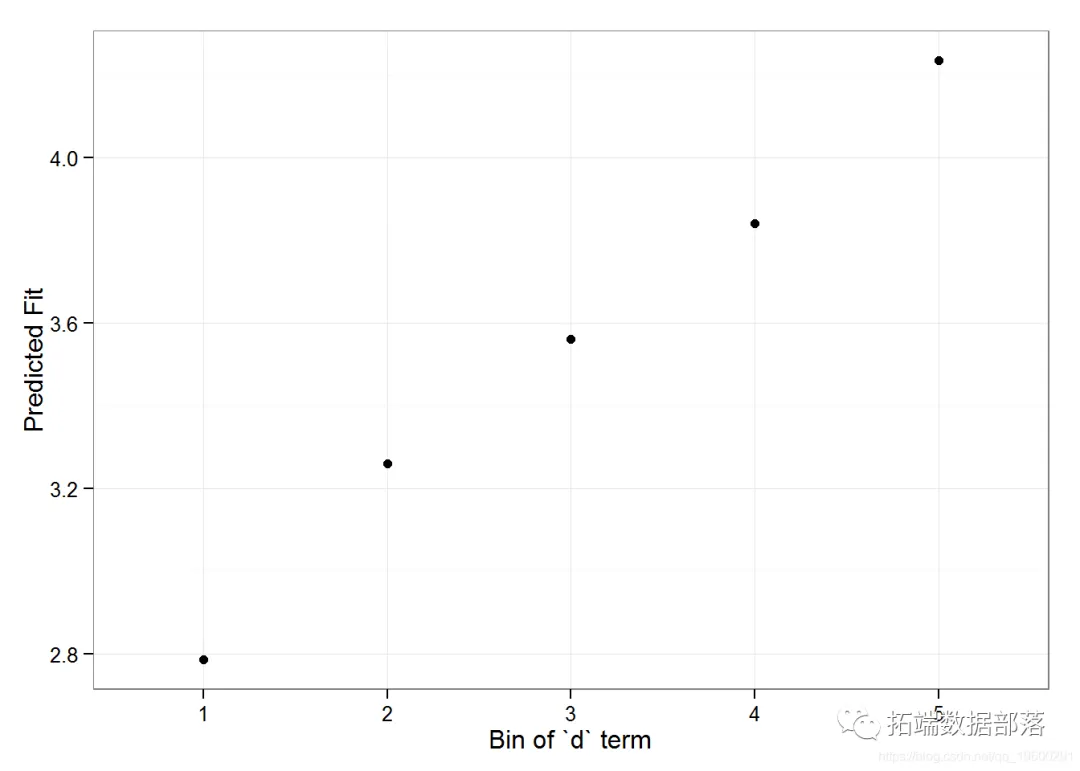 02  03  04 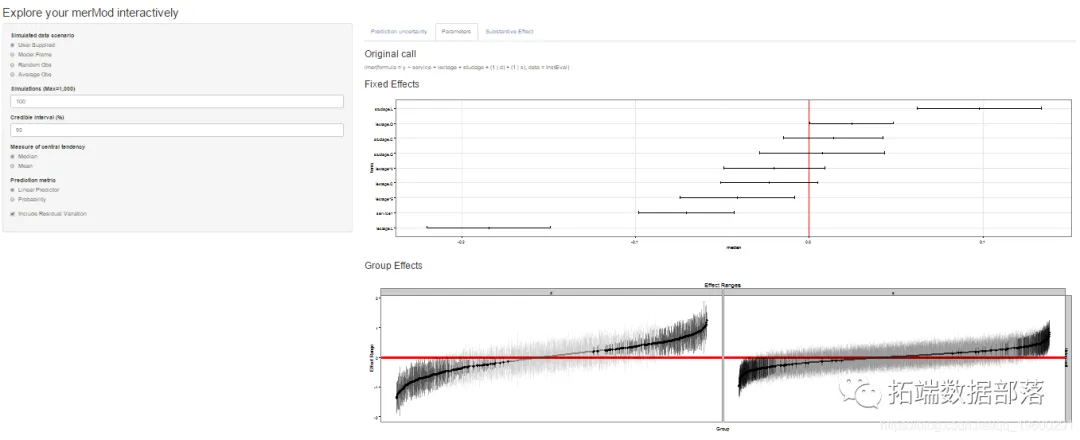 代码语言:javascript复制
# 展示数据的前几行以确认数据加载正确
head(data)
# 第一部分:拟合GLMM
# 随机截距模型
summary(mod_lmer1) # 查看模型摘要
# 随机斜率和截距模型
summary(mod_lmer2) # 查看模型摘要
# 第二部分:GLMM假设检验
# 检查随机效应的方差成分是否显著
Anova(mod_lmer1, type="II Wald") # 使用Anova函数进行方差分析
# 检查残差的正态性、同方差性等假设
plot(mod_lmer1) # 绘制模型诊断图
# 第三部分:模型选择
# 使用AIC进行模型选择
AIC(mod_lmer1, mod_lmer2)
# 第四部分:从GLMM中得出推论
# 获取固定效应的系数估计和置信区间
# 获取随机效应的方差估计
VarCorr(mod_lmer2)
# 绘制模型预测图
library(ggplot2)
ggplot 代码语言:javascript复制
# 展示数据的前几行以确认数据加载正确
head(data)
# 第一部分:拟合GLMM
# 随机截距模型
summary(mod_lmer1) # 查看模型摘要
# 随机斜率和截距模型
summary(mod_lmer2) # 查看模型摘要
# 第二部分:GLMM假设检验
# 检查随机效应的方差成分是否显著
Anova(mod_lmer1, type="II Wald") # 使用Anova函数进行方差分析
# 检查残差的正态性、同方差性等假设
plot(mod_lmer1) # 绘制模型诊断图
# 第三部分:模型选择
# 使用AIC进行模型选择
AIC(mod_lmer1, mod_lmer2)
# 第四部分:从GLMM中得出推论
# 获取固定效应的系数估计和置信区间
# 获取随机效应的方差估计
VarCorr(mod_lmer2)
# 绘制模型预测图
library(ggplot2)
ggplot
geom_smooth函数在ggplot2中默认不支持lmer模型,你可能需要手动计算预测值并添加到数据框中,或者使用其他包(如ggeffects或effects)来生成预测值并绘制图形。 另外,关于嵌套和交叉随机效应的问题,lme4包中的lmer函数支持拟合这些复杂的随机效应结构。你可以通过在公式中指定适当的随机效应项来实现这一点。例如,对于嵌套随机效应,你可以使用(1|Group1/Group2);对于交叉随机效应,你可以使用(1|Group1) + (1|Group2)。具体的随机效应结构取决于你的研究设计和假设。 展示了如何模拟固定效应和混合效应模型的数据,并比较了这两种模型的拟合结果。您的目标是展示固定效应模型和混合效应模型之间的区别,并通过绘图来可视化这些差异。然而,从您提供的模拟数据和结果来看,没有明显的差异是可见的,这可能是因为模拟的数据没有表现出强烈的随机效应。 添加一些额外的解释和可视化步骤,以帮助更好地理解固定效应和混合效应模型之间的区别。 代码语言:javascript复制 plot(fitted(m_lme), resid(m_lme)) qqnorm(resid(m_lme)) qqline(resid(m_lme)) # 添加参考线 qqnorm(ranef(m_lme)[, 1]) qqline(ranef(m_lme)[, 1]) # 添加参考线 plot(x, resid(m_lme)) # 固定效应模型拟合图 pal |
【本文地址】
今日新闻 |
推荐新闻 |