Surv单因素批量生存分析使用 cox批量生存回归分析有点像deseq2的design差异分析designG:\r\2021 |
您所在的位置:网站首页 › 单因素cox回归分析和km分析 › Surv单因素批量生存分析使用 cox批量生存回归分析有点像deseq2的design差异分析designG:\r\2021 |
Surv单因素批量生存分析使用 cox批量生存回归分析有点像deseq2的design差异分析designG:\r\2021
|
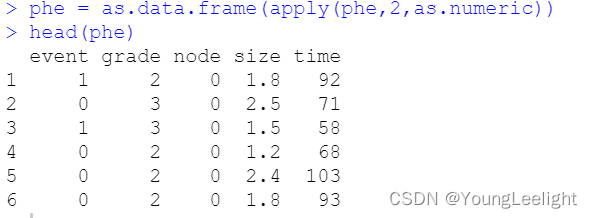
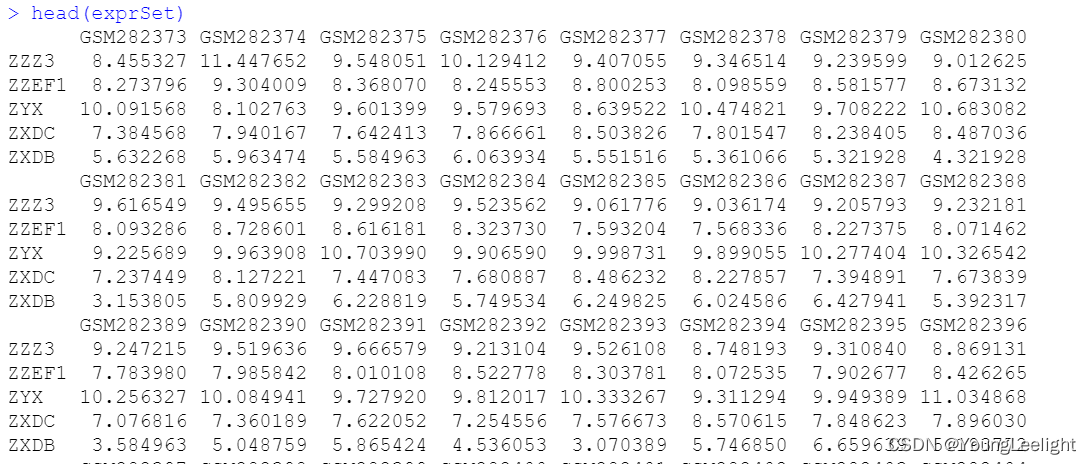
批量生存分析 input codes output input: 表达矩阵 和 meta 信息 表达矩阵
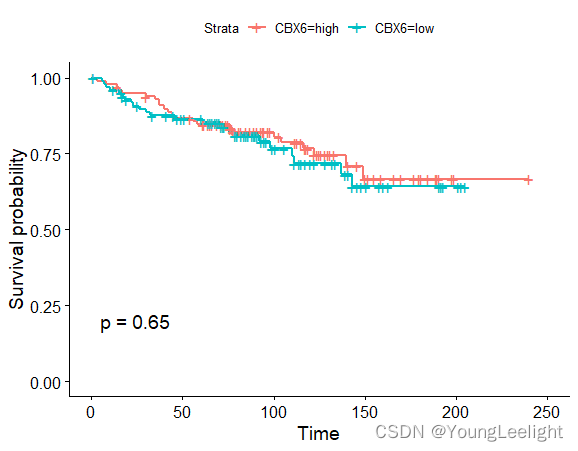
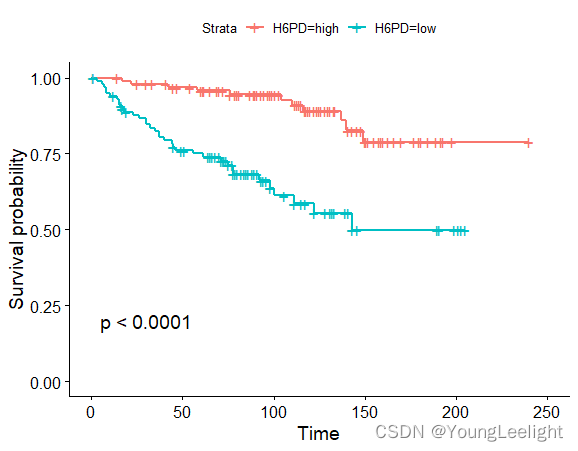
存活分析 library(survival) library(survminer) # 利用ggsurvplot快速绘制漂亮的生存曲线图 sfit median(exprSet['CBX4',]),'high','low') head(phe) table(phe$CBX4) ggsurvplot(survfit(Surv(time, event)~CBX4, data=phe), conf.int=F, pval=TRUE) phe$CBX6=ifelse(exprSet['CBX6',]>median(exprSet['CBX6',]),'high','low') head(phe) table(phe$CBX6) ggsurvplot(survfit(Surv(time, event)~CBX6, data=phe), conf.int=F, pval=TRUE)
head(log_rank_p) ZZZ3 ZZEF1 ZYX ZXDC ZXDB ZWINT 0.15685996 0.29704979 0.01703644 0.08484583 0.33396320 0.03875669
可以找到p值最小的为 HDP6基因
###这样就可以得到既能跟grade相关,又有临床预后意义的基因啦。 批量生存分析 使用 coxph 回归方法 因为cox可以进行多因素回归分析 colnames(phe) head(phe) mySurv=with(phe,Surv(time, event)) cox_results median(gene),'high','low') survival_dat |
【本文地址】
今日新闻 |
推荐新闻 |
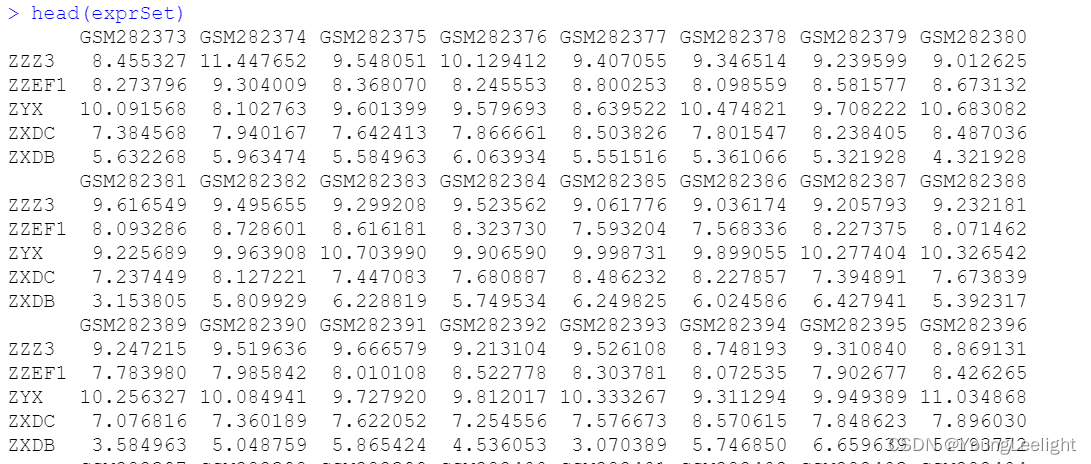 meta信息
meta信息