群体遗传学 |
您所在的位置:网站首页 › 克格勃超能档案选择消除记忆 › 群体遗传学 |
群体遗传学
|
一、选择消除分析
所谓选择性清除:当一个有利突变发生后,这个突变基因的适合度越高,就越容易被选择固定。当这个基因被快速固定之后,与此基因座连锁的染色体区域,由于搭车效应也被固定下来,大片紧密连锁的染色体区域因此失去多态性,这种由于搭车效应引起多态性下降的现象,遗传上称为选择清除。 群体进化选择消除分析:简单的说就是基因组某区域由于受到了选择而消除多态性。选择消除分析是正向选择在物种基因组上留下的印迹。与野生祖先相比,栽培或驯化的物种发生选择消除的区域遗传多样性显著降低,这是驯化区域的典型特征。 下图可以形象的展示受选择后的结果。
选择消除分析可以做什么? 挖掘人工驯化过程中受选择的基因,如家猪与肉质相关的基因,大豆中与油含量相关的基因。挖掘物种适应性进化中受选择的基因,如藏猪的高原适应性,毛果杨高低纬度气候适应性。 二、常见名词A、Ka/Ks The ratio of the number of nonsynonymous substitutions per nonsynonymous site (Ka) to the number of synonymous substitutions per synonymous site (Ks)。其中: Ks = 同义突变SNP数/同义位点数, 即同义突变率 Ka = 非同义突变SNP数/非同义位点数, 即非同义突变率 Ka/Ks >> 1,基因受正选择(positive selection) Ka/Ks =1,基因中性进化(neutral evolution) Ka/Ks 0,表明存在大量的中等频率的等位基因,这可能是由于群体瓶颈效应,群体结构,或者平衡选择引起的。 如果Tajima’s D< 0,表明存在大量的低频等位基因位点。Tajima’s D分析表示中性进化,越偏离0,受选择程度越高。 E、XP-CLR :全称是 the cross-population composite likelihood ratio test(跨群体复合似然比检验),是一种是基于选择清除(selective sweep)的似然方法。XP-CLR 利用了两个群体之间的多基因座等位基因频率差异(multilocus allele frequency differentiation)建立模型,使用布朗运动来模拟中性下的遗传漂移,并使用确定性模型来近似地对附近的单核苷酸多态性(SNPs)进行选择性扫描。 三、选择消除分析常用的方法1、基于群体分化(Fst) 群体的固定系数F反映了群体等位基因杂合性水平。固定系数F是F统计量(Fst)的一个特例。Fst分析表示群体的分化程度,值越大,群体分化程度越高,受选择程度越高。 Fst分布图,横坐标代表不同的染色体名称,纵坐标代表相应染色体窗口内Fst值,另外的两条虚线代表两种选择阈值(top 5%或1%)。 (1) Fst挖掘人工驯化过程中受选择的基因 74份中国李核心种质可聚类为南、北、东北及国外品种群,南方品种群较为原始,遗传多样性丰富,且与其他品种群间存在基因交流,推测中国李起源于我国南方长江流域。不同品种群间进行选择压分析,共鉴定到35个受选择位点,其中,开花调控、抗病抗逆及类黄酮代谢等重要途径关键基因显著富集,初步揭示了中国李重要性状驯化的分子基础 纵坐标如Fst(F_S),表示该结果是F群体与S群体间的分化指数,这里对Fst做了一个Z变换,所以数值范围不是[0~1],但值越大也是分化越显著区域。图上可直观看到分化指数较高的位置。 (2) 挖掘物种适应性进化中受选择的基因–野外收集到的各亚种间在遗传物质上有何差异,不妨来看看借助选择性清除探究“只有长江江豚可以在淡水中生活的奥秘”? 采用Sweep Finder2软件基于CLR(复合似然比),来探测群体内的选择信号,鉴定出39 个具有强选择性扫描信号的 CLR 峰,宽、窄脊江豚分别鉴定出218 个和 144 个候选基因。 为什么本文选择CLR来进行,原因在于常用于选择性清除的分析如FST适合物种内,不适合物种间、而Ka/Ks整合难度大,故本文采用了优化后的SFS原理。如果您的样本于此类似,不妨参考参考。 (3) XP-CLR、π、Tajima’s D多种参数结合的选择性分析结果 栽培苹果具有人工驯化的很多痕迹,特别是其中的果实重量、硬度、甜度、酸度等。通过XP-CLR、π、Tajima’s D相结合的方法定位到6号染色体上的包含9个基因的区域内。 上图a中灰色背景点表示起源于其他野生祖先而不是来自比较的基因组,绿色的线为XP-CLR前1%的分位数。 2、基于群体多样性分析 π用来分析碱基多态性,多态性越低,受选择程度越高。 3、基于群体中性进化的分析 在标准中性进化模型下,Tajima’s D 的理论值为零。如果Tajima’s D 值为正,表明存在大量的中等频率的等位基因,这可能是由于群体瓶颈效应,群体结构,或者平衡选择引起的。如果 Tajima’s D 值为负,表明存在大量的低频等位基因位点。Tajima’s D分析表示中性进化,越偏离0,受选择程度越高。 1、Fst和θπ 的结合 Fst 和θπ已被证实是一种很有效力地检测选择消除区域的方法,特别是在挖掘与生存环境密切相关的功能区时,往往可以得到较强的选择信号,图5为Fst与θπ选择消除分析结果展示,二者共同筛选较强的选择信号,便于目标基因的筛选。 横坐标为θπ 的比值(驯化/野生),纵坐标为Fst值,分别对应上面的频率分布图和右侧的频率分布图,中部的点图则代表不同窗口内的相应的Fst和θπ 比值。其中最上方蓝色和绿色区域为θπ选择出来的top 5%区域,红色区域为Fst所选择top 5%区域,中间蓝色和绿色区域为Fst和θπ的交集,即为候选的位点。 2、Tajima’s D和θπ的结合
横坐标为θπ 值,纵坐标为Tajima’s D值,分别对应上面的频率分布图和右侧的频率分布图,中部的点图则代表不同窗口内的相应的θπ和Tajima’s D值。其中蓝色区域为θπ选择出来的top 5%区域,绿色区域为Tajima’s D选择出的top 5% 区域,红色箭头所指的区域为θπ和Tajima’s D的交集,即为候选的位点。 3、Fst和Hp的结合
如何看懂这张图: 横坐标表示染色体上的某个区间,纵坐标表示Hp、Fst,图中的蓝点表示杂合率(Hp),图中的橙黄色点表示固定系数(Fst)。通常选择杂合率Hp较小,群体分化系数Fst较大的点,图中两虚线间的点即为候选位点。 参考文献: [1] Hufford M B, Xu X, van Heerwaarden J,et al. Comparative population genomics of maize domestication andimprovement. Nature Genetics, 2012, 3(6),44(7): 808-11. [2] Qiu Q, Wang L, Wang K,et al. Yak whole-genome resequencing reveals domestication signatures and prehistoricpopulation expansions. Nature Communications, 2015,22(12), 6:10283. [3] Li M,Tian S,Jin L,et al. Genomic analyses identify distinct patterns of selection in domesticatedpigs and Tibetan wild boars. Nature Genetics, 2013,45(12): 1431-8. [4] Axelsson E, Ratnakumar A, Arendt M L,et al. The genomic signature of dog domestication reveals adaptation to astarch-rich diet. Nature, 2013 Mar 21(3),495(7441): 360-4. [5]Sun, X., Jiao, C., Schwaninger, H. et al. Phased diploid genome assemblies and pan-genomes provide insights into the genetic history of apple domestication. Nat Genet 52, 1423–1432 (2020). [6] Huang Z , Shen F , Chen Y , et al. Chromosome-scale Genome Assembly and Population Genomics Provide Insights into the Adaptation, Domestication, and Flavonoid Metabolism of Chinese Plum[J]. The Plant Journal, 2021. |
【本文地址】
今日新闻 |
推荐新闻 |





 π结果分析图中,横轴表示基因组的位置,纵坐标表示π值,图中的曲线表示3个群体的多态性水平。群体π值反映了群体基因组碱基多样性。
π结果分析图中,横轴表示基因组的位置,纵坐标表示π值,图中的曲线表示3个群体的多态性水平。群体π值反映了群体基因组碱基多样性。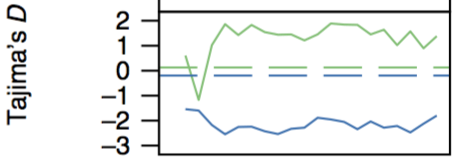
 如何看懂这张图:
如何看懂这张图: 如何看懂这张图:
如何看懂这张图: