手把手教你处理illumina beadchip芯片数据 |
您所在的位置:网站首页 › illumina测序数据分析流程R语言 › 手把手教你处理illumina beadchip芯片数据 |
手把手教你处理illumina beadchip芯片数据
|
欢迎关注”生信修炼手册”! 在NAD+代谢相关的文献中,使用了两批illumina beadchip的芯片数据进行分析,本文以其中一篇数据为例,详细展示该平台的数据处理流程。 GSE112676包含741个样本的全血基因表达谱数据,链接如下 https://www.ncbi.nlm.nih.gov/geo/query/acc.cgi?acc=GSE112676 该数据的处理流程在以下文献中有详细描述 https://translational-medicine.biomedcentral.com/articles/10.1186/s12967-019-1909-0
可以分为以下几步 1. 下载GenomeStudio导出的数据 GenomeStudio是处理illumina原始芯片的软件,在数据库中提供了该批数据的导出结果
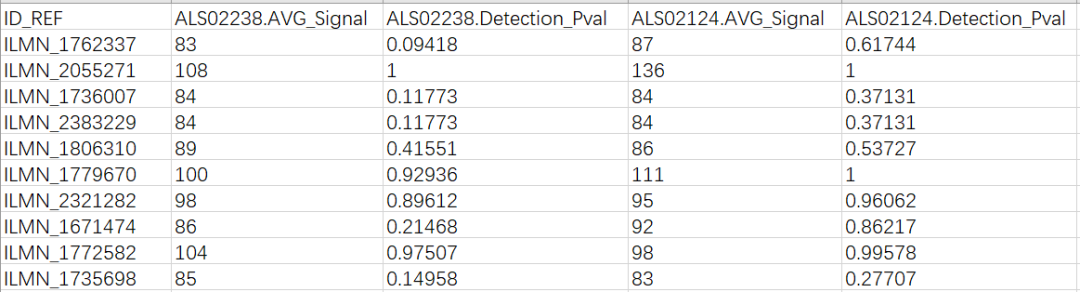
该文件的内容如下
每一行为一个探针,每个样本用两列表示,第一列是AVG_Signal, 表示探针的荧光信号强度,第二列为Detection_Pval, 表示检测信号的p值。 2. 进行pvalue 的校正 计算荧光信号强度与检测p值的相关性,代码如下 > x sample_cnt # 计算pvalue 和 intensity 之间的相关性 > spearman_cor # 统计相关系数的分布 > length(spearman_cor[spearman_cor > 0.9]) [1] 221 > length(spearman_cor[spearman_cor < -0.9]) [1] 520可以看到,正如文章中所说,520个样本的相关性小于-0.9, 221个样本的相关性大于0.9, 整体样本分为明显的两类,一类正相关,一列负相关。为了使整体保持一致,将占比较少的正相关样本的p值,改为1-P, 代码如下 > # 校正p值 > for(t in which(spearman_cor > 0.9)) { + x[[t * 2]] # 校正后重新查看相关系数的分布 > spearman_cor > length(spearman_cor[spearman_cor > 0.9]) [1] 0 > length(spearman_cor[spearman_cor < -0.9]) [1] 741可以看到,校正之后,所有的样本都为负相关。 3. 背景校正和归一化 文献中描述的方法如下
使用limma包进行处理,背景校正选择normexp方法,归一化选择quantile方法,代码如下 > # 读取 illumina beadchip, 读取校正后的数据 > RG # 背景校正 normal–exponential convolution model > RG # quantile 归一化 > RG dim(RG) [1] 48803 741预处理之后,得到了741个样本共48803个探针水平的表达量。 4. 提取基因水平的表达量 由于一个基因对应多个探针,在该文献中,只使用表达量最高的探针作为该基因的表达量。以上就是一个完整的illumina芯片的数据处理流程。 ·end· —如果喜欢,快分享给你的朋友们吧— 原创不易,欢迎收藏,点赞,转发!生信知识浩瀚如海,在生信学习的道路上,让我们一起并肩作战! 本公众号深耕耘生信领域多年,具有丰富的数据分析经验,致力于提供真正有价值的数据分析服务,擅长个性化分析,欢迎有需要的老师和同学前来咨询。 更多精彩 KEGG数据库,除了pathway你还知道哪些 全网最完整的circos中文教程 DNA甲基化数据分析专题 突变检测数据分析专题 mRNA数据分析专题 lncRNA数据分析专题 circRNA数据分析专题 miRNA数据分析专题 单细胞转录组数据分析专题 chip_seq数据分析专题 Hi-C数据分析专题 HLA数据分析专题 TCGA肿瘤数据分析专题 基因组组装数据分析专题 CNV数据分析专题 GWAS数据分析专题 机器学习专题 2018年推文合集 2019年推文合集 2020推文合集 写在最后 转发本文至朋友圈,后台私信截图即可加入生信交流群,和小伙伴一起学习交流。 扫描下方二维码,关注我们,解锁更多精彩内容!
一个只分享干货的 生信公众号 |
【本文地址】
今日新闻 |
推荐新闻 |