如何查看目标基因在不同组织和细胞中的表达情况及基因组信息? |
您所在的位置:网站首页 › consensus怎么用 › 如何查看目标基因在不同组织和细胞中的表达情况及基因组信息? |
如何查看目标基因在不同组织和细胞中的表达情况及基因组信息?
|
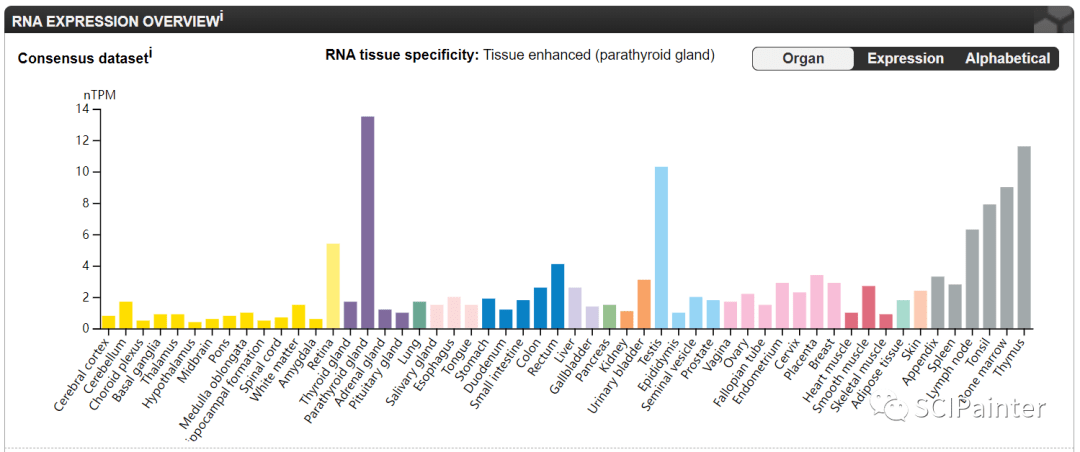
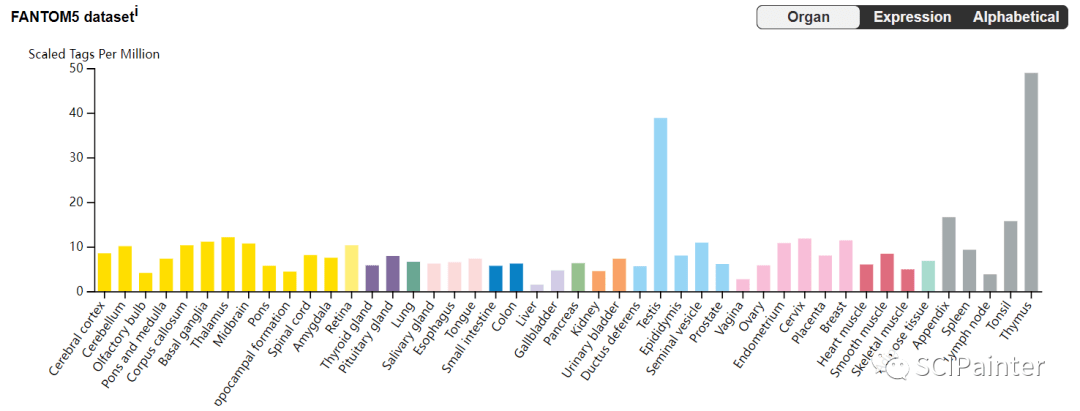
1. HPA(人类蛋白质图谱):https://www.proteinatlas.org/ 2. UCSC 基因组浏览器:http://www.genome.ucsc.edu/index.html 3. TIMER2.0:http://timer.cistrome.org/ 图A:C1ORF112在人类正常组织中的表达情况 打开HPA数据库,检索目标基因C1ORF112,如下。
点击Tissue。 页面下翻即可获得图A。Consensus dataset是基于HPA和GTEx两个数据库来源的人类正常组织的RNA-seq测序共识数据集,展示了C1ORF112在人类不同正常组织中的表达情况,不同颜色代表不同器官,比如黄色的柱子为脑部相关组织的表达。
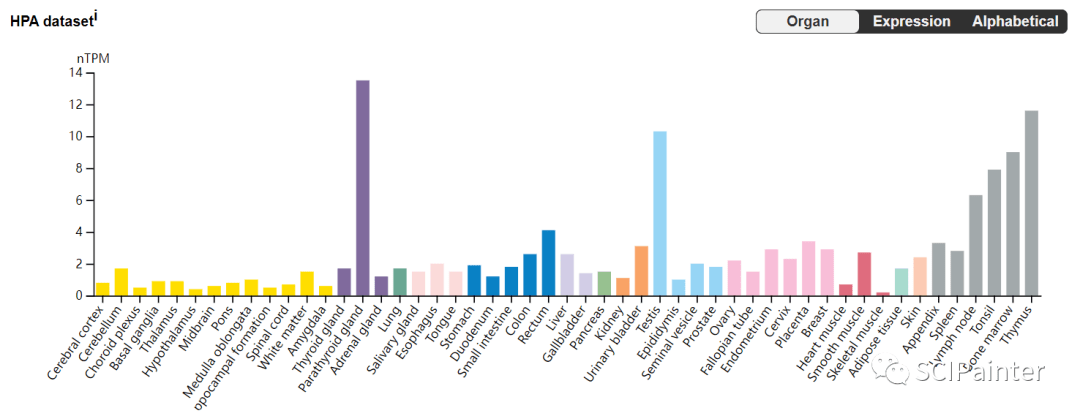
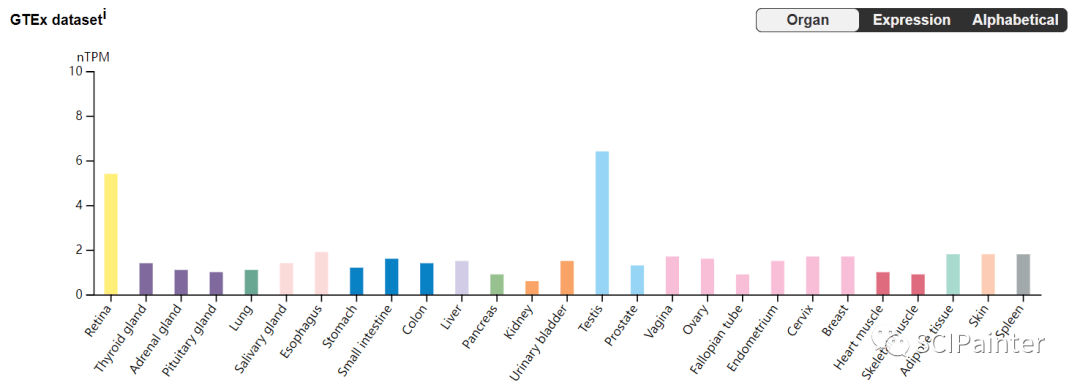
基于HPA、GTEx、FANTOM5单个数据集的组织表达柱形图在文章中作为补充图表,我们也都能在同一页面获取。
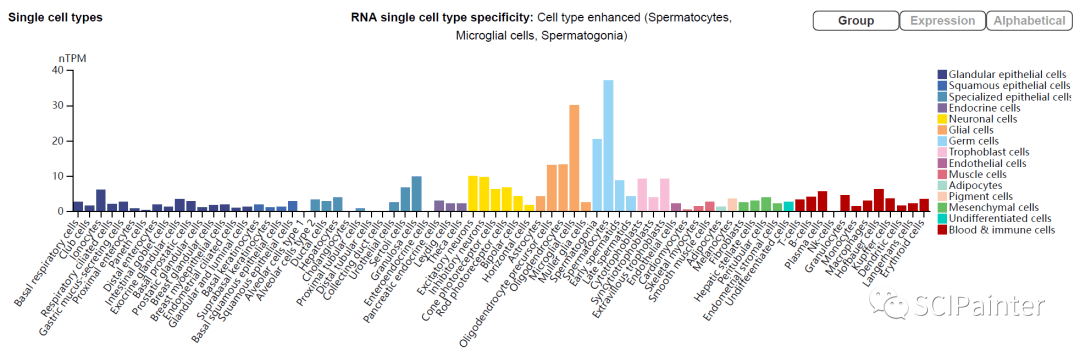
想查看C1ORF112在各细胞类型中的表达情况,可以通过点击网页顶部的单细胞Single cell type(第三个)。 页面下拉即可获取,下图也作为了论文补充图表提供。
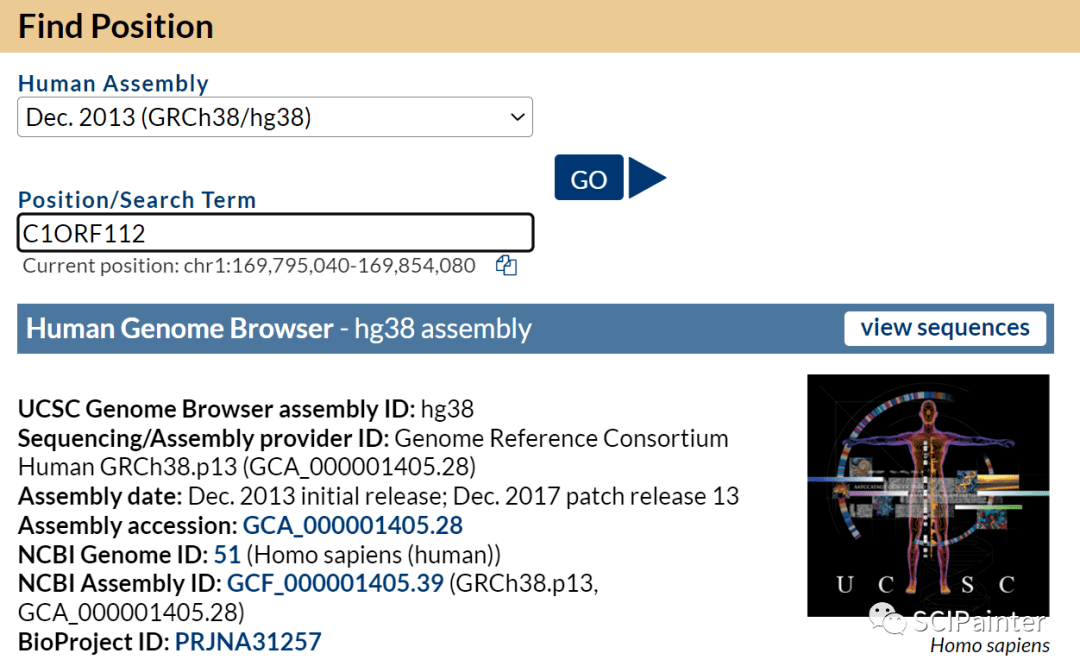
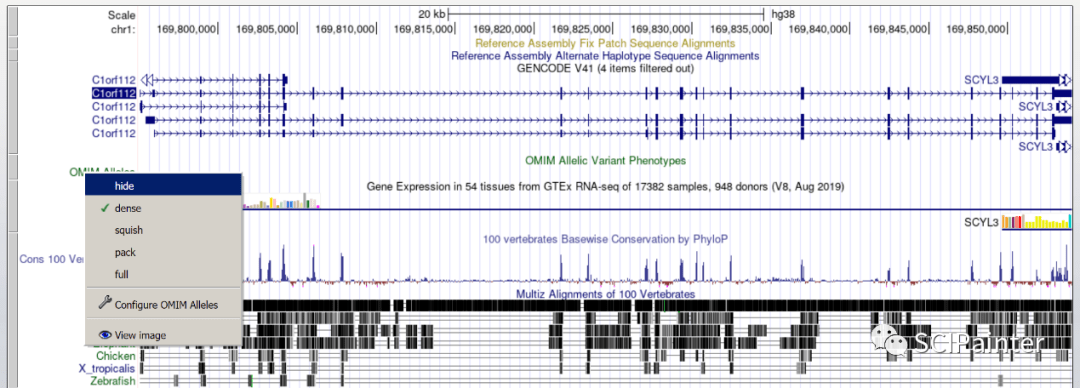
图B:C1ORF112基因保守分析 进入UCSC浏览器首页,点击右侧的Genome Browser。
选择人类基因组版本(测序项目一般选择hg38),并输入目标基因C1ORF112,点击GO。
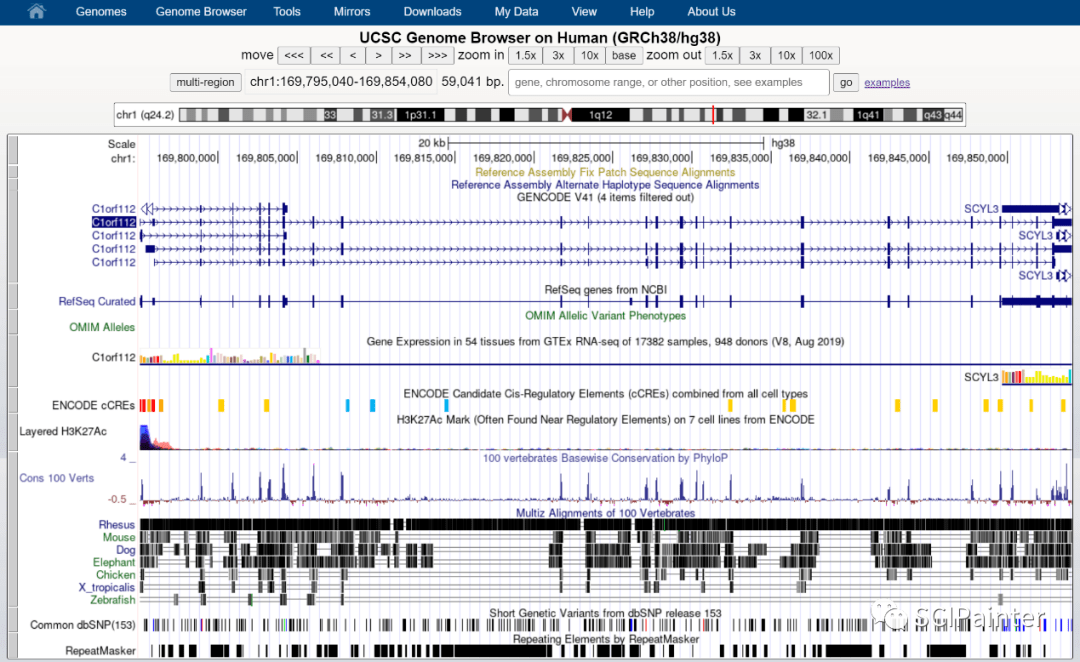
即可展示基因组相关信息,目前是一个默认的展示配置,控制版块在页面下方,相关内容可以按需进行添加和隐藏,点击refresh即可刷新,这里复现不需要我们就不再展示了。
不需要的信息我们也可以通过将鼠标右击,选择hide进行快速隐藏。
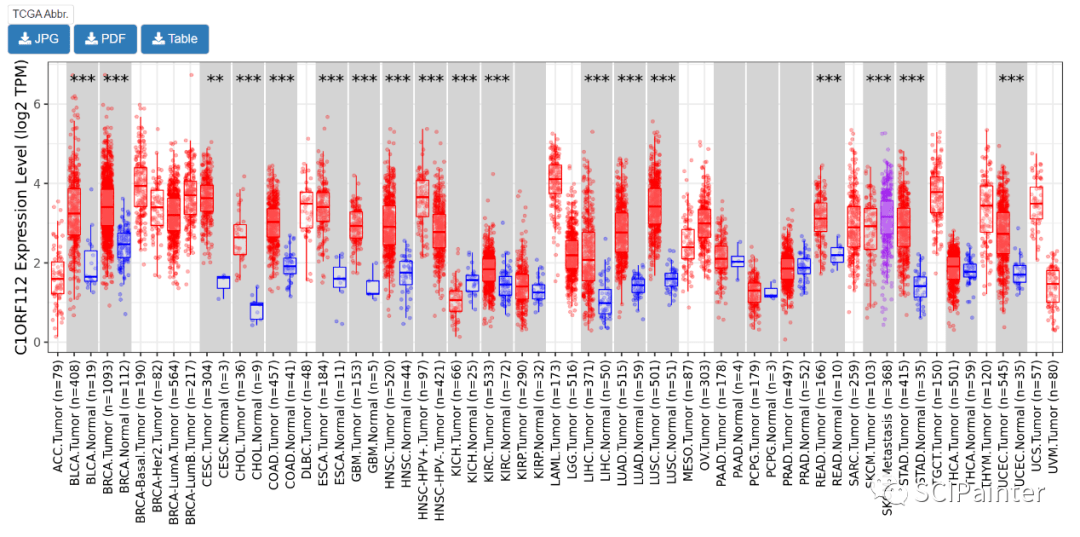
最后通过网页顶部菜单栏View—PDF/PS输出矢量图表。 图C:C1ORF112基因在不同类型肿瘤中的表达情况 进入TIMER2.0首页,选择Cancer Exploration—Gene_DE。
输入目标基因C1ORF112。
即可显示C1ORF112在TCGA的不同类型肿瘤中的表达情况,以及tumor和normal表达是否有显著差异(红tumor,绿normal,部分白底表示缺乏normal的RNA-seq测序数据)。
关于HPA和TIMER2.0的具体使用我们往期也有介绍,具体有兴趣可戳: 《分享一个人类蛋白图册数据库》 《免疫浸润神器更新!TIMER2.0使用指南》 好啦,今天的分享就到这里! 参考文献 Chen J, Mai H, Chen H, et al. Pan-Cancer Analysis Identified C1ORF112 as a Potential Biomarker for Multiple Tumor Types[J]. Frontiers in Molecular Biosciences, 2021, 8. *未经许可,不得以任何方式复制或抄袭本篇文章之部分或全部内容。版权所有,侵权必究。 基迪奥生物|专业定制测序服务 联系方式:020-39341079;[email protected]返回搜狐,查看更多 |
【本文地址】
今日新闻 |
推荐新闻 |